文章信息
- 吴双胜, 孙瑛, 窦相峰, 任振勇, 张姣姣, 贾蕾, 杨鹏, 庞星火.
- Wu Shuangsheng, Sun Ying, Dou Xiangfeng, Ren Zhenyong, Zhang Jiaojiao, Jia Lei, Yang Peng, Pang Xinghuo
- 北京市3起新型冠状病毒Omicron变异株聚集性疫情的感染来源和传播链分析
- Analysis on infection sources and transmission chains of three outbreaks caused by 2019-nCoV Omicron variant in Beijing, China
- 中华流行病学杂志, 2023, 44(3): 373-378
- Chinese Journal of Epidemiology, 2023, 44(3): 373-378
- http://dx.doi.org/10.3760/cma.j.cn112338-20221112-00966
-
文章历史
收稿日期: 2022-11-12
2. 北京市疾病预防控制中心办公室, 北京 100013
2. Central Office, Beijing Municipal Center for Disease Prevention and Control, Beijing 100013, China
新型冠状病毒(新冠病毒)Omicron变异株是继Alpha、Beta、Gamma、Delta之后的第五种国际关切的新冠病毒变异株,且Omicron变异株及其各分支自2022年以来成为主导毒株,且潜伏期、代间距等流行病学特征发生改变[1]。2022年1月北京市报告首起Omicron变异株聚集性疫情,并导致多起本土疫情[2]。“外防输入、内防反弹”是我国防控新冠病毒的总策略,新冠病毒感染防控方案明确指出接触被病毒污染的物品后可造成感染[3]。有研究显示,新冠病毒存活时间与温度、物品材质等环境因素相关[4-5],在低温条件下存活时间较长,国内已发现多起冷链物品导致的本土疫情[6];在常温条件下存活时间相比低温条件更短,但也有研究提示常温物品导致新冠病毒传播[7]。本研究旨在对2022年1-4月北京市3起可能由常温物品通过跨境物流途径导致的新冠病毒Omicron变异株聚集性疫情进行调查,分析其感染来源和传播链,为今后新冠病毒感染疫情防控提供参考依据。
对象与方法1. 研究对象:为2022年1-4月北京市3起新冠病毒Omicron变异株聚集性疫情涉及的所有确诊病例或无症状感染者,3起疫情分别有6、42和32例感染者。每起疫情根据感染者网络直报的报告时间先后进行编码。
2. 研究方法:
(1)相关定义:①确诊病例、无症状感染者、密切接触者(密接)、密接的密接(次密)、临床分型和聚集性疫情:见《新型冠状病毒肺炎防控方案(第八版)》[3],感染者包括确诊病例和无症状感染者。②发现方式:主动检测包括因出京、就诊等需求的愿检尽检人员;主动就诊指因发热等症状就诊于医疗机构。③潜伏期:感染新冠病毒至发病的间隔时间,对明确单次暴露的病例计算潜伏期,潜伏期=发病日期-暴露日期。④代间距:原发病例的发病日期与其续发病例发病日期的间隔时间,对单次单源暴露病例计算代间距,代间距=第n+1代发病时间-第n代发病时间。
(2)流行病学调查:通过流行病学调查和大数据技术对所有新冠病毒感染者进行活动轨迹核查,对活动轨迹涉及的风险点位进行密接判定。流行病学调查方法依据《新型冠状病毒肺炎防控方案(第八版)》[3]。
(3)实验室检测:①应用实时荧光定量PCR进行新冠病毒核酸检测,主要针对新冠病毒基因组中开放读码框1ab(ORF1ab)和核壳蛋白N。②应用全基因组测序技术对阳性人员和环境标本进行测序,将测序结果与近期输入病例和本土病例序列进行比对。③应用化学发光法进行血清IgM、IgG抗体检测。实验室检测流程和结果判定依据《新型冠状病毒肺炎防控方案(第八版)》[3]。
(4)感染来源分析:考虑病例发病时间、排毒周期、接触时间、接触方式、接触地点,对流行病学调查、大数据分析比对和基因测序结果进行综合分析,明确该起疫情的感染来源,梳理病例之间的传播链。感染来源调查技术路线与北京市新发地市场、顺义区、大兴区局部地区等其他新冠病毒感染聚集性疫情近似[8-10]。
3.统计学分析:使用WPS Office软件进行数据录入、整理和绘图。采用描述性流行病学方法,对本起聚集性疫情相关病例的时间、地区和人群分布进行描述,分析重点病例流行病学史以及病例之间的传播链,并绘制病例传播关系图。符合正态分布的计量数据以x±s表示,非正态分布的计量资料以M(Q1,Q3)表示,计数资料以例(%)表示。
结果1. 疫情基本情况:2022年1-4月北京市发现3起Omicron变异株聚集性疫情,累计报告80例感染者,分别报告6、42、32例新冠病毒感染者,其中1起感染来源可能为国际邮件,2起为进口衣物,分别对3起疫情的6、9、18例病例阳性标本进行基因测序分析,病毒基因序列分别为Omicron变异株BA.1、BA.1.1、BA.2分支。见表 1。
(1)国际邮件关联疫情:2022年1月14日通过主动检测初筛阳性,发现疫情,1月15日网络直报,疫情持续8 d,累计报告6例感染者。现住址涉及1个区、2个乡镇/街道。男性1例,女性5例;≤17岁1例、18~59岁5例;家务及待业人员1例、散居儿童1例、干部职员4例。
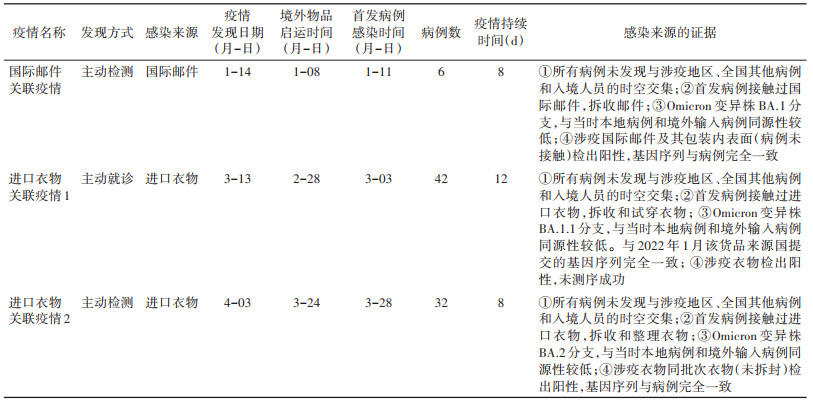
(2)进口衣物关联疫情1:2022年3月13日通过主动就诊,检测初筛阳性,发现疫情,3月14日网络直报,疫情持续12 d,累计报告42例感染者。见图 1。现住址涉及4个区、11个乡镇/街道。男性17例,女性25例;年龄M(Q1,Q3)为40(33,60)岁,其中≤17岁9例、18~59岁22例、≥60岁11例;餐饮食品业服务人员8例、干部职员6例、工人1例、离退休人员14例、商业服务人员4例、学生9例。
|
| 图 1 2022年3月一起进口衣物相关Omicron变异株聚集性疫情的报告时间和发病时间 |
(3)进口衣物关联疫情2:2022年4月3日通过主动检测初筛阳性,发现疫情,4月4日网络直报,疫情持续8 d,累计报告32例感染者。见图 2。现住址涉及4个区、12个乡镇/街道。男性14例,女性18例;年龄M(Q1,Q3)为30(26,40)岁,其中≤17岁4例、18~59岁26例、≥60岁2例;商业服务人员15例、干部职员5例、家务及待业人员3例、餐饮食品业服务人员、幼托儿童、农民各2例,教师、清洁工、散居儿童各1例。

|
| 图 2 2022年4月一起进口衣物相关Omicron变异株聚集性疫情的报告时间和发病时间 |
2. 感染来源与传播链:
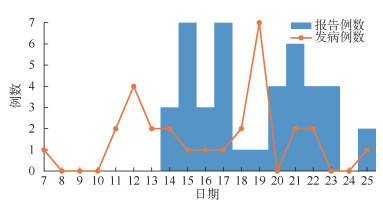
(1)国际邮件关联疫情:感染来源为国际邮件的可能性较大(表 1)。所有病例未发现与涉疫地区、全国其他病例和入境人员的时空交集。病例阳性标本基因序列一致,且均与当时本地病例和境外输入病例基因序列同源性较低。采集国际邮件外包装、内表面和内部纸张22件涂抹标本,其中2件包装外表面、2件内表面和8件文件内纸张标本经检测为阳性,其中外包装内表面(病例未接触)阳性标本测序成功,与病例基因序列一致。2022年1月8日涉疫国际邮件从境外启运,1月11日首发病例拆收、接触该涉疫邮件,其他病例未接触该邮件。首发病例1月13日发病,14日检出阳性(Ct值:ORF1ab为29、N为29)。首发病例造成2个传播支链,涉及5例续发病例。传播支链1:病例2为同住人员。支链2:病例3为首发病例同楼层同事,病例4、5、6与其同住感染。见图 3。
|
| 图 3 2022年1月一起国际邮件相关Omicron变异株聚集性疫情的传播链 |
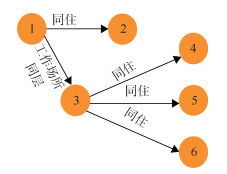
(2)进口衣物关联疫情1:感染来源为网购的进口衣物可能性大(表 1)。所有病例未发现与涉疫地区、全国其他病例和入境人员的时空交集。病例阳性标本的基因序列一致,且均与当时本地病例和境外输入病例基因序列同源性较低。采集进口衣物外表面和内表面涂抹标本各1件,其中1件阳性,未测序成功。2022年2月28日涉疫进口衣物从境外启运,3月3日首发病例拆收、试穿、接触该涉疫进口衣物,之后未接触,其他病例未接触该进口衣物。首发病例3月7日发病,13日检出阳性(Ct值:ORF1ab为30、N为31)。首发病例造成41例续发病例,涉及某小学和某烤鸭店聚集性疫情。传播支链1:首发病例到某烤鸭店就餐造成12例续发、同桌就餐4例感染、同时段就餐2例感染、工作人员6例续发。支链2:首发病例造成同住病例8、9感染。支链3:病例17造成同住病例18感染。支链4:病例25、27造成亲属5例感染。支链5:病例30造成同楼层同事1例和同班车1例感染,继而导致同班车病例的同住2例感染。支链6:病例28造成同单元病例33及同住1例感染。支链7:病例9造成同住3例感染。支链8:病例8造成其小学同学6例及相关同学同住3例感染。支链9:病例4通过物品携带在一培训班造成病例23感染,继而导致其同住2例感染。见图 4。
|
| 注:同一方框里为同一家庭或单位的病例;粉色为首发病例,橙色为续发病例 图 4 2022年3月一起进口衣物相关Omicron变异株聚集性疫情的传播链 |
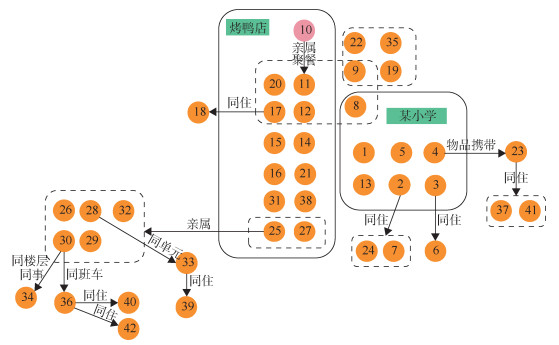
(3)进口衣物关联疫情2:感染来源为网购的进口衣物可能性大(表 1)。所有病例未发现与涉疫地区、全国其他病例和入境人员的时空交集。病例阳性标本的基因序列一致,与当时本地病例和境外输入病例基因序列同源性较低。涉疫批次进口衣物已销售完毕,采集某物流点尚未派发处理、且同一来源地进口衣物183件涂抹标本,检出10件阳性,其中1件衣物外表面阳性标本测序成功,与病例基因序列一致。2022年3月24日涉疫进口衣物从境外启运,首发病例为某服装店店员,负责拆包装,3月28日直接接触该涉疫进口衣物,其他病例未接触该批次进口衣物的包装。首发病例4月1日发病,3日检出阳性(Ct值:ORF1ab为29、N为29)。首发病例造成31例续发病例,涉及某服装店、某城中村、某幼儿园、某医院聚集性疫情。传播支链1:首发病例在某服装店工作期间造成同事9例和顾客3例感染,3例同事病例分别导致同住1例续发。支链2:首发病例造成某城中村同住人员5例及其邻居2例感染。支链3:病例11、23在隔离期间分别造成病例29、30感染。支链4:病例5为某幼儿园儿童,导致同学2例感染,继而导致其同住3例感染。支链5:病例14在购买早餐期间造成某医疗机构工作人员病例27感染,继而导致其同住1例感染。见图 5。

|
| 注:同一方框里为同一家庭或单位的病例;粉色为首发病例,橙色为续发病例 图 5 2022年4月一起进口衣物相关Omicron变异株聚集性疫情的传播链 |
3. 潜伏期和代间距:13例病例有明确单次暴露时间,潜伏期1~6 d,M(Q1,Q3)为3(2,4)d。对单次单源暴露的20例续发病例进行分析,代间距1~5 d,M(Q1,Q3)为3(2,4)d。
讨论本研究对2022年1-4月3起新冠病毒Omicron变异株聚集性疫情的感染来源和传播链进行分析,发现3起疫情可能由常温进口物品经跨境物流引入。既往关于进口冷链物品关联疫情的报告较多[6],且有研究从冷链物品分离出活病毒[11],但是关于常温进口物品导致疫情的研究较少[2]。本研究提示可能通过常温进口物品传播Omicron变异株,主要依据:第一,3起疫情的首发病例及其他病例均未发现与涉疫地区、全国其他病例和入境人员的同时空交集,同时3起疫情病例基因测序结果均与当时本地病例和境外输入病例同源性较低,基本排除通过人际传播引入的可能。第二,3例首发病例均有明确的常温进口物品接触史,其他病例未直接接触涉疫物品。第三,其中2起疫情的涉疫相关物品基因序列与病例完全一致。据此认为,对2022年1月国际邮件、2022年4月进口衣物相关疫情的感染来源调查中流行病学史、人和物品基因测序结果等证据较充分;2022年3月另一起进口衣物相关疫情的涉疫物品未成功测序,但与2022年1月该货品来源国提交的基因序列完全一致。
新冠病毒存活时间与温度、湿度、材质等因素相关[4-5],有研究显示室温条件下在大多物体表面存活时间短于24 h,但在车厘子、猪肉表面存活时间超过24 h,随着温度降低存活时间显著增长[7]。本研究发现3起Omicron变异株疫情相关的进口物品均为常温物品,境外启运至首发病例感染的时间间隔为3~4 d,提示北半球1-4月Omicron变异株存活时间可达3 d。可能原因:第一,Omicron变异株感染者的排毒量高于其他变异株,有研究显示Omicron变异株感染者在住院第一周的平均呼吸排放率是Delta变异株感染者的约5倍[12];第二,北半球1-4月气温还处于较低状态;第三,有研究显示Omicron变异株在物体表面存活时间长于其他毒株[13]。上述3个因素增加接触被Omicron变异株污染物品造成感染的风险。疫情高发期间(尤其是低温季节)尽量减少购买境外物品,若收到境外物品时,要佩戴口罩和一次性手套,做好消毒和手卫生,避免直接接触涉疫物品。
Omicron变异株潜伏期、代间距等流行病学特征发生改变[1]。本研究发现中国北京市Omicron变异株代间距、潜伏期M(Q1,Q3)均为3(2,4)d,与中国河南省对于Omicron变异株BA.2.2分支聚集性疫情的研究结果一致,代间距、潜伏期M(Q1,Q3)分别为3(2,3)d、3(2,4.25)d[14];短于Delta变异株及其他早期毒株,中国宁波市2021年Delta变异株潜伏期为4.0(3.0,5.8)d、代间距为3.5(2.0,5.3)d[15],中国北京市2020年早期毒株潜伏期为5(3.5,7.5)d、代间距为5(3.5,11.5)d[16],中国广州市2020年早期疫情、非洲地区入境关联疫情和Delta变异株关联疫情潜伏期分别为6.5(4.0,10.8)d、4.0(2.5,6.0)d和4.0(3.0,5.0)d,代间距分别为4.0(3.0,8.0)d、4.0(2.5,6.0)d和3.0(2.0,5.0)d[17]。一项系统综述也比较了Omicron和Delta变异株的代间距和潜伏期,代间距分别为3.1(95%CI:2.9~3.2)d、3.4(95%CI:3.0~3.7)d,潜伏期分别为3.6(95%CI:2.3~4.9)d、4.8(95%CI:3.9~5.6)d,与本研究结果基本一致[18]。研究结果提示,Omicron变异株潜伏期短、代间距短、传播速度快,需要加强疫情调查处置速度,加快做好风险区域管控和风险人群排查。
综上,本研究发现3起可能由常温进口物品导致的Omicron变异株聚集性疫情,提示常温货品通过跨境物流途径输入Omicron变异株疫情的风险,疫情高发期间收取境外物品时应做好防护,避免直接接触涉疫物品。Omicron变异株代间距、潜伏期M(Q1,Q3)均为3(2,4)d,短于Delta变异株,提示Omicron变异株传播速度更快,应加快流行病学调查处置,做到以快制快。
利益冲突 所有作者声明无利益冲突
作者贡献声明 吴双胜:实施研究、数据收集、论文撰写、经费支持;孙瑛、窦相峰、任振勇、张姣姣、贾蕾:实施研究、数据整理、统计学分析;杨鹏、庞星火:研究指导、论文修改、经费支持
志谢 感谢北京市疾病预防控制中心和东城区、海淀区和朝阳区疾病预防控制中心现场调查组和检测组以及市级流行病学调查人员所做的贡献
| [1] |
吴俣, 刘珏, 刘民, 等. 新型冠状病毒Omicron变异株的流行病学特征及防控研究[J]. 中国全科医学, 2022, 25(1): 14-19. Wu Y, Liu J, Liu M, et al. Epidemiologic features and containment of SARS-CoV-2 Omicron Variant[J]. Chin Gen Pract, 2022, 25(1): 14-19. DOI:10.12114/j.issn.1007-9572.2021.00.348 |
| [2] |
Zhang DT, Wu SS, Ren ZY, et al. A local cluster of omicron variant COVID-19 likely caused by internationally mailed document — Beijing Municipality, China, January 2022[J]. China CDC Wkly, 2022, 4(14): 302-304. DOI:10.46234/ccdcw2022.031 |
| [3] |
国务院应对新型冠状病毒肺炎疫情联防联控机制综合组. 关于印发新型冠状病毒肺炎防控方案(第八版)的通知[EB/OL]. (2021-05-14)[2022-10-12]. http://www.nhc.gov.cn/jkj/s3577/202105/6f1e8ec6c4a540d99fafef52fc86d0f8.shtml.
|
| [4] |
Chin AWH, Chu JTS, Perera MRA, et al. Stability of SARS-CoV-2 in different environmental conditions[J]. Lancet Microbe, 2020, 1(1): e10. DOI:10.1016/S2666-5247(20)30003-3 |
| [5] |
Geng YS, Wang YC. Stability and transmissibility of SARS-CoV-2 in the environment[J]. J Med Virol, 2023, 95(1): e28103. DOI:10.1002/jmv.28103 |
| [6] |
Wang JH, Li FQ, Liu ZP, et al. COVID-19 outbreaks linked to imported frozen food in China: status and challege[J]. China CDC Wkly, 2022, 4(22): 483-487. DOI:10.46234/ccdcw2022.072 |
| [7] |
李夫, 徐柯, 潘阳, 等. 食品和加工材料表面SARS-CoV-2存活规律研究[J]. 国际病毒学杂志, 2022, 29(3): 204-209. Li F, Xu K, Pan Y, et al. Persistence of SARS-CoV-2 on surfaces of food and processing materials[J]. Int J Virol, 2022, 29(3): 204-209. DOI:10.3760/cma.j.issn.1673-4092.2022.03.006 |
| [8] |
Pang XH, Ren LL, Wu SS, et al. Cold-chain food contamination as the possible origin of COVID-19 resurgence in Beijing[J]. Natl Sci Rev, 2020, 7(12): 1861-1864. DOI:10.1093/nsr/nwaa264 |
| [9] |
吴双胜, 潘阳, 段玮, 等. 北京市一起境外输入无症状感染者相关新冠肺炎聚集性疫情的溯源调查[J]. 国际病毒学杂志, 2021, 28(3): 187-191. Wu SS, Pan Y, Duan W, et al. Tracing infection source of an outbreak in Beijing caused by an imported asymptomatic case of COVID-19[J]. Int J Virol, 2021, 28(3): 187-191. DOI:10.3760/cma.j.issn.1673-4092.2021.03.003 |
| [10] |
吴双胜, 马春娜, 张莉, 等. 全国首起新型冠状病毒Alpha变异毒株相关本地疫情的溯源调查[J]. 中华预防医学杂志, 2021, 55(11): 1311-1315. Wu SS, Ma CN, Zhang L, et al. Survey on source of infection of the first local outbreak caused by SARS-CoV-2 Alpha variant in China[J]. Chin J Prev Med, 2021, 55(11): 1311-1315. DOI:10.3760/cma.j.cn112150-20210727-00710 |
| [11] |
Ma HL, Wang ZG, Zhao X, et al. Long distance transmission of SARS-CoV-2 from contaminated cold chain products to humans-Qingdao city, Shandong province, China, September 2020[J]. China CDC Wkly, 2021, 3(30): 637-644. DOI:10.46234/ccdcw2021.164 |
| [12] |
Liu LN, Guo ZD, Sevalie S, et al. Comparison of the amount of SARS-CoV-2 exhaled by delta and omicron patients[J]. J Infect, 2022, 85(5): 573-607. DOI:10.1016/j.jinf.2022.08.028 |
| [13] |
Hirose R, Itoh Y, Ikegaya H, et al. Differences in environmental stability among SARS-CoV-2 variants of concern: both omicron BA. 1 and BA. 2 have higher stability[J]. Clin Microbiol Infect, 2022, 28(11): 1486-1491. DOI:10.1016/j.cmi.2022.05.020 |
| [14] |
潘静静, 王莹莹, 王文华, 等. 一起由奥密克戎变异株BA. 2.2引起的河南省新冠肺炎本土疫情流行病学特征分析[J]. 中国公共卫生, 2022, 38(8): 975-979. Pan JJ, Wang YY, Wang WH, et al. Epidemiological characteristics of a local COVID-19 outbreak caused by Omicron (BA. 2.2) variant in Henan province[J]. Chin J Public Health, 2022, 38(8): 975-979. DOI:10.11847/zgggws1138726 |
| [15] |
陈奕, 闫克栋, 张栋梁, 等. 新型冠状病毒Delta变异株引起的宁波市镇海区本土疫情传播链分析[J]. 中华流行病学杂志, 2022, 43(7): 1044-1048. Chen Y, Yan KD, Zhang DL, et al. Transmission chains of local epidemic of COVID-19 caused by 2019-nCoV Delta variant in Zhenhai district, Ningbo[J]. Chin J Epidemiol, 2022, 43(7): 1044-1048. DOI:10.3760/cma.j.cn112338-20220214-00116 |
| [16] |
孙亚敏, 刘锋, 蔡伟, 等. 北京市海淀区新型冠状病毒肺炎疫情初期聚集性疫情特征分析[J]. 国际病毒学杂志, 2022, 29(2): 155-158. Sun YM, Liu F, Cai W, et al. Characteristics of clustered outbreaks in the early stage of COVID-19 epidemic in Haidian district, Beijing[J]. Int J Virol, 2022, 29(2): 155-158. DOI:10.3760/cma.j.issn.1673-4092.2022.01.015 |
| [17] |
赵文恒, 马钰, 汪慧, 等. 广州市3起本地新型冠状病毒肺炎疫情流行特征及分析[J]. 中华流行病学杂志, 2021, 42(12): 2088-2095. Zhao WH, Ma Y, Wang H, et al. Epidemiological characteristics of three local epidemics of COVID-19 in Guangzhou[J]. Chin J Epidemiol, 2021, 42(12): 2088-2095. DOI:10.3760/cma.j.cn112338-20210728-00592 |
| [18] |
Du ZW, Liu CF, Wang L, et al. Shorter serial intervals and incubation periods in SARS-CoV-2 variants than the SARS-CoV-2 ancestral strain[J]. J Travel Med, 2022, 29(6): taac052. DOI:10.1093/jtm/taac052 |
 2023, Vol. 44
2023, Vol. 44