文章信息
- 桂滔, 贾磊, 韩静婉, 鲍作义, 刘思扬, 李敬云, 李林.
- Gui Tao, Jia Lei, Han Jingwan, Bao Zuoyi, Liu Siyang, Li Jingyun, Li Lin.
- 北京男男性行为人群HIV-1序列和流行趋势分析
- Analysis on gene sequence of HIV isolated from men who have sex with men in Beijing
- 中华流行病学杂志, 2015, 36(9): 988-993
- Chinese Journal of Epidemiology, 2015, 36(9): 988-993
- http://dx.doi.org/10.3760/cma.j.issn.0254-6450.2015.09.017
-
文章历史
- 投稿日期: 2015-02-10
近年来,我国HIV/AIDS病例数逐年上升,HIV感染途径也逐渐变化。性传播,包括异性性传播和同性性传播,成为HIV感染的主要途径。监测数据显示,MSM导致HIV感染快速上升。MSM导致的HIV感染在2005年仅占报告病例的0.3%,2009年为14.7%,2011年上升至17.4%。在2011年新发感染中,MSM导致的HIV感染高达29.4%[1],同性性传播已成为我国HIV传播的主要途径之一。
北京作为中国的政治、文化、经济中心,外来人口和流动人口多,MSM人群估计数也高于其他城市。研究显示,北京MSM中HIV-1的感染率在2002年时为3.1%[2],2006年升至4.8%[3],2010年则达到6%左右,明显高于其他城市。近年来,针对北京MSM人群HIV流行特征的研究越来越多,但多为血清学和简单分子流行病学研究,本研究拟利用Bayesian进化理论重建北京地区MSM人群中HIV系统发育关系,进行群体动态研究,深入分析北京MSM人群中流行的HIV毒株与其他毒株的关系,阐明北京地区MSM人群中流行毒株动态变化过程,为艾滋病行为干预提供切入点,为我国艾滋病防控工作提供数据信息。 材料与方法
1. 序列来源:研究中北京MSM人群流行的部分HIV毒株序列由本实验室获得,其他序列均来自Los Alamos HIV Database(www.hiv.lanl.gov)。选择的序列信息包含取样时间、取样城市、传播途径以及序列的亚型。所有序列经过初步整理后选择最终序列。
2. 系统发育树:使用muscle v3.1.1软件对序列进行比对,BioEdit 7.1.1软件对序列进行编辑校正,jModel Test v0.1[4]软件选择分析序列的碱基替代模型,PhyML 3.0软件aLRT SH-Like方法构建系统发育树[5, 6]。
3. Bayesian coalescent Markov Chain Monte Carlo(MCMC)进化分析:使用BEAST软件分析,根据jModel Test运算结果选择碱基替代模型,根据Bayesian因子选择分子钟模型,MCMC链计算80 000 000次,每8 000次取样[7, 8]。运算结果使用Tracer v1.5软件分析,使用TreeAnnotator v1.7.5软件构建Maximum clade credibility tree(MCC树),使用FigTree 1.3.1软件查看和编辑MCC树。 结 果
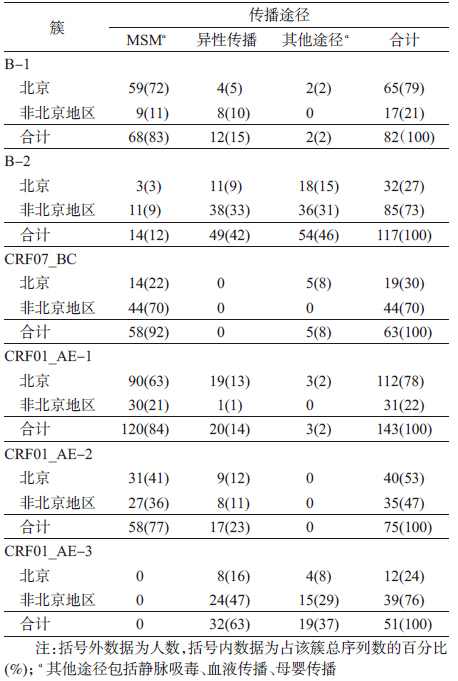
1. 序列收集和分析数据系列的建立:本实验室共获得北京MSM人群中HIV gag区基因序列80条,包含CRF01_AE亚型、CRF07_BC亚型、B亚型毒株。检索数据库,发现位于HIV基因组的906~1 446位(使用国际标准株HXB2定位)的基因序列最多。通过整理下载序列合并实验室已有序列,共获得来自中国背景信息明确的HIV基因序列778条,包含CRF01_AE亚型、CRF07_BC亚型、B亚型。其中北京MSM人群HIV-1基因序列237条、北京市其他传播途径人群HIV-1基因序列114条,非北京地区MSM人群HIV-1基因序列166条、非北京地区其他传播途径人群HIV-1基因序列261条(表 1)。共收集北京MSM人群的HIV-1毒株基因序列(gag区540 bp)237条,其中,CRF01_AE亚型毒株为151条(占63.7%);CRF07_BC亚型毒株为19条(占8.0%);B亚型毒株为67条(占28.3%)。
2. 进化关系分析:为了解北京MSM人群与异地MSM人群、其他传播途径人群间HIV-1的进化关系,将获得的778条序列与Los Alamos HIV Database中A~J、CRF01_AE、CRF07_BC、CRF08_BC共19条国际标准亚型参考序列进行系统进化分析,构建ML系统发育树(图 1)。将系统发育树中SH值≥90%[5]且序列数量≥40条定义为簇,将北京MSM序列占总序列数≥40%的簇定义为北京MSM簇。本研究共发现6个大簇,包括B亚型2个簇、CRF07_BC重组型1个簇、CRF01_AE重组型3个簇。分析显示:B亚型的2个簇分别为欧美B亚型和Thai B亚型,来自北京MSM的序列只有3例位于Thai B亚型簇中,其他全部位于欧美B亚型簇(占该簇序列数的72%)中,说明北京MSM人群中流行的B亚型毒株与我国有偿献血人群中流行的B亚型毒株不同,而与欧美等国家MSM人群中流行的B亚型毒株相似,提示二者具有很近的亲缘关系。在CRF01_AE亚型的3个簇中,北京MSM人群的序列全部位于CRF01_AE-1和CRF01_AE-2簇。分析显示,CRF01_AE-1和CRF01_AE-2簇均是以MSM人群序列为主(分别占84%和77%),但CRF01_AE-1簇中北京MSM所占比例(90条,63%)高于CRF01_AE-2簇(31条,41%),差异有统计学意义(P≤0.05,χ2=9.2972)。见表 2。
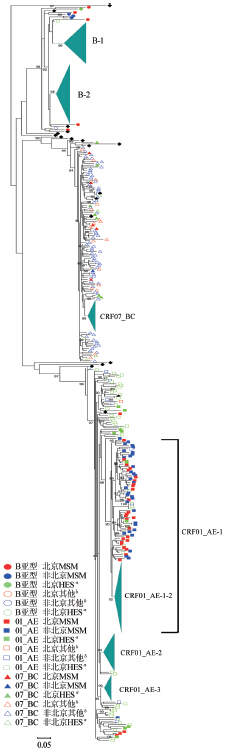 |
| 注:a 异性传播; b 其他传播途径,包括静脉吸毒、血液传播、母婴传播 图 1 PhyML 3.0 aLRT SH-like构建ML系统发育树 |
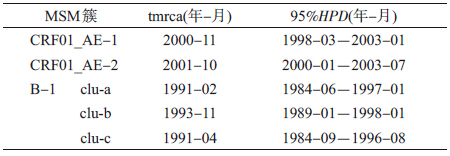
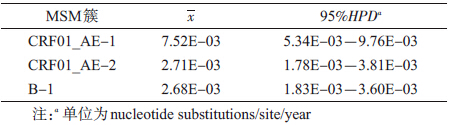
3. 进化特征:HIV进化特征分析可以有效的追溯其传入时间,研究传播事件对疫情的影响。本研究利用BEAST 1.7.5软件计算以北京MSM人群HIV毒株为主的3个传播簇的突变速率与祖先毒株传入时间(the time of most recent common ancestor,tMRCA)。结果显示:CRF01_AE两簇传入北京MSM人群的时间均为2001年左右(表 3、图 2),但两簇的突变速率存在明显差异,CRF01_AE-1簇突变速率为7.52E-03(nucleotide substitutions/site/year),95%HPD(highest posterior density)为5.34E-03~9.76E-03,明显高于其他两簇(表 4)。针对B-1簇的分析显示:欧美B亚型毒株是通过3次独立事件传入北京MSM人群(在进化树中分为3小簇),传入时间分别为1991年3月(1984年7月至1997年2月)、1994年1月(1990年5月至1999年3月)、1994年12月(1989年5月至1998年4月),但3簇的突变速率差异无统计学意义。
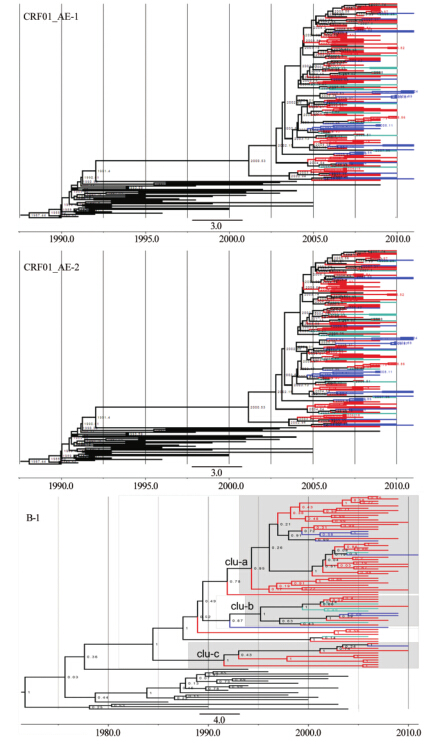 |
| 注:红色树枝为北京MSM、蓝色树枝为非北京地区MSM、蓝绿色树枝为北京其他传播途径;灰色底纹标注3次输入事件为clu-a、clu-b、clu-c,后验概率≥95% 图 2 BEAST 1.7.5构建MCC树,推断CRF01_AE-1、CRF01_AE-2、B-1北京MSM簇tMRCA |
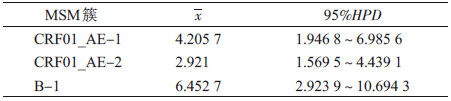
4. 流行特征分析:基于合并理论的系统进化分析可以根据序列重塑流行历史。本研究使用Bayesian Skyline模型[9],重塑北京MSM人群HIV毒株的流行历史,使用Birth-Death Basic Reproductive Number模型[10]分析了各簇毒株流行人群再生指数(Reproductive Number,R0),以推断各簇毒株流行对北京MSM人群HIV流行的影响。Bayesian Skyline Plot结果显示:CRF01_AE-1簇的感染人群在2005-2007年间出现了快速增长,而CRF01_AE-2簇的感染人群一直处于平稳状态,B-1簇在2005年以后也一直处于相对平稳状态(图 3),说明CRF01_AE-1簇毒株对于2005年之后北京MSM人群中HIV的播散贡献较大。Birth-Death Basic Reproductive Number模型推断北京MSM簇的再生指数显示:CRF01_AE-1簇的R0值为4.205 7(95%CI:1.946 8~6.985 6),明显大于CRF01_AE-2簇的2.921(95%CI:1.569 5~4.439 1)(表 5),也说明CRF01_AE-1簇的传播速度要快于CRF01_AE-2簇。
 |
| 注:虚线之间为两簇同一时间段内群体动态变化情况 图 3 BEAST 1.7.5重建CRF01_AE-1、CRF01_AE-2、B-1北京MSM簇群体动态 |
本文利用Bayesian合并理论、系统发育等生物信息学方法对北京MSM人群中HIV-1流行情况进行分析,这种基于序列的分析方法可以减小抽样误差导致的结果偏倚,更深层次的挖掘该人群中HIV-1流行特点。合并理论是一个分析子代与祖先关系的模型,在大群体中依靠少量样本推断遗传谱系的分布以及群体历史,同时作为一个非连续的至简的假设自然进化的遗传谱系模型在Bayesian 分析中常作为先验使用[9, 11, 12]。Bayesian Evolutionary Analysis by Sampling Trees(BEAST)是一款基于Bayesian合并理论利用MCMC算法分析基因序列的软件平台[13, 14]。本文运用BEAST分析北京MSM人群中HIV-1的流行及进化特征,通过北京MSM人群的基因序列推断这个群体的进化历史以及群体动态。
男男性行为是HIV传播的主要高危行为之一,针对MSM人群的防控对有效控制HIV播散有重要意义。我国MSM人群估计超过1 800万人[15],而且该人群中HIV-1感染率高达6.5%[16],阐明该人群中HIV的亚型分布、传播方式和流行趋势可以为我国艾滋病防控提供重要信息。分子流行病学研究显示我国主要流行HIV-1毒株为CRF07_BC、CRF08_BC、CRF01_AE以及B’亚型。早期研究表明,我国MSM人群中主要流行毒株为CRF07_BC、CRF01_AE以及B亚型,B亚型毒株为优势毒株。本研究发现:CRF01_AE是北京MSM人群中流行的HIV-1主要基因型(63.7%),其所占比例显著高于B亚型(28.3%)。在本研究中,系统进化分析显示B亚型毒株传入北京MSM人群的时间较早(20世纪90年代初期),但增长速度较慢,而且在2005年左右B亚型毒株在北京MSM人群中开始处于平稳状态;CRF01_AE亚型毒株则出现快速增长,并最终取代B亚型毒株成为优势毒株,有力佐证了之前Wang等[17]的研究结论。
20世纪90年代初期CRF01_AE亚型毒株由越南、缅甸经性传播与静脉吸毒传播进入我国云南省、广西壮族自治区,然后主要通过异性传播向东南沿海和西南边境扩散[18, 19, 20, 21, 22]。性传播是CRF01_AE亚型毒株最主要的传播方式。本研究中北京MSM序列全位于CRF01_AE-1簇与CRF01_AE-2簇,说明该簇之中其他人群与北京MSM人群联系紧密存在流行病学联系,特别是异性性传播人群,提示毒株可能通过异性性传播向普通人群扩散。CRF07_BC簇中北京MSM的序列与来自其他传播途径的HIV序列交错在一起,提示CRF07_BC毒株在MSM人群中尚未形成局部的快速传播。我国MSM人群由于受道德观念、家庭压力、社会意识等影响,部分人群呈现双性恋,增加了普通人群感染HIV-1的风险,使得防控形势也更加复杂。
MSM人群与其他艾滋病高危人群不同,在其人群内传播已不受地域限制。研究发现以北京MSM人群为主的HIV毒株簇中也包含辽宁、河北、河南、安徽、江苏等地MSM人群,以省份为单位划分的空间已经不足以完全区分MSM人群特征,MSM人群的这种迁徙特征加大了HIV-1统筹防控的难度。针对毒株簇的深入分析显示:尽管CRF01_AE-1簇与CRF01_AE-2簇主要由北京MSM人群组成(表 2),但CRF01_AE-1簇中北京MSM人群比例更高、异性传播人群比例更低,说明当地MSM人群更倾向于单性恋。根据对突变速率推算,CRF01_AE-1簇突变速率明显高于CRF01_AE-2簇,说明该簇人群中HIV-1 CRF01_AE毒株受到的免疫压力更大,发生的传播事件更多。再生指数的计算则证实了这个推论,CRF01_AE-1簇人群再生指数显著大于CRF01_AE-2簇,说明在取样的时间段内CRF01_AE-1簇中HIV-1 CRF01_AE毒株产生了更大的流行。群体动态重建中CRF01_AE-1簇人群在2005-2007年间发生快速上升,印证了CRF01_AE-1簇感染人群较CRF01_AE-2簇增长迅速的推论。综上,深入分析CRF01_AE-1簇人群的流行病学特点并对其进行有针对性的行为干预,对减少北京市MSM人群中HIV的传播有重要意义。
| [1] Ministry of Health of the People's Republic of China,UNAIDS,World Health Organization. 2011 estimates for the HIV/AIDS epidemic in China[J]. Chin J AIDS STD,2012,18(1):1-5. (in Chinese) 中华人民共和国卫生部,联合国艾滋病规划署,世界卫生组织. 2011年中国艾滋病疫情估计[J]. 中国艾滋病性病,2012,18(1):1-5. |
| [2] Choi KH, Liu H, Guo YQ, et al. Emerging HIV-1 epidemic in China in men who have sex with men[J]. Lancet,2003,361(9375):2125-2126. |
| [3] Li SW, Zhang XY,Li XX,et al. Detection of recent HIV-1 infections among men who have sex with men in Beijing during 2005-2006[J]. Chin Med J,2008,121(12):1105-1108. |
| [4] Posada D. jModel Test:Phylogenetic model averaging[J]. Mol Biol Evol,2008,25(7):1253-1256. |
| [5] Guindon S,Delsuc F,Dufayard JF,et al. Estimating maximum likelihood phylogenies with phyML[M]//Posada D. Bioinformatics for DNA Sequence Analysis. Humana:Humana Press,2009:113-137. |
| [6] Guindon S, Dufayard JF,Lefort V,et al. New algorithms and methods to estimate maximum-likelihood phylogenies:assessing the performance of phyML 3.0[J]. Syst Biol,2010,59(3):307-321. |
| [7] Drummond AJ,Ho SYW,Phillips MJ,et al. Relaxed phylogenetics and dating with confidence[J]. PLoS Biol,2006,4(5):e88. |
| [8] Suchard MA, Weiss RE, Sinsheimer JS. Bayesian selection of continuous-time Markov chain evolutionary models[J]. Mol Biol Evol,2001,18(6):1001-1013. |
| [9] Drummond AJ,Rambaut A,Shapiro B,et al. Bayesian coalescent inference of past population dynamics from molecular sequences[J]. Mol Biol Evol,2005,22(5):1185-1192. |
| [10] Stadler T,Kouyos R,Von Wyl V,et al. Estimating the basic reproductive number from viral sequence data[J]. Mol Biol Evol,2012,29(1):347-357. |
| [11] Drummond A,Pybus OG,Rambaut A. Inference of viral evolutionary rates from molecular sequences[J]. Adv Parasitol,2003,54:331-358. |
| [12] Wakeley J. Coalescent theory has many new branches[J]. Theor Popul Biol,2013,87:1-4. |
| [13] Drummond AJ, Rambaut A. BEAST :Bayesian evolutionary analysis by sampling trees[J]. BMC Evol Biol,2007,7(1):214-218. |
| [14] Drummond AJ,Suchard MA,Xie D,et al. Bayesian Phylogenetics with BEAUti and the BEAST 1.7[J]. Mol Biol Evol,2012,29(8):1969-1973. |
| [15] Shang H,Xu JJ,Han XX,et al. Bring safe sex to China[J]. Nature,2012,485(7400):576-577. |
| [16] Ministry of Health of the People's Republic of China. 2012 China AIDS response progress report[R]. Beijing:Other Organisations and Agencies,2012. |
| [17] Wang WH,Xu JQ,Jiang SL,et al. The dynamic face of HIV-1 subtypes among men who have sex with men in Beijing,China[J]. Curr Hiv Res,2011,9(2):136-139. |
| [18] Liao HN, Tee KK,Hase S, et al. Phylodynamic analysis of the dissemination of HIV-1 CRF01_AE in Vietnam[J]. Virology,2009,391(1):51-56. |
| [19] Chen J,Young NL,Subbarao S,et al. HIV type 1 subtypes in Guangxi province,China,1996[J]. AIDS Res Hum Retroviruses,1999,15(1):81-84. |
| [20] Yu XF,Chen J,Shao YM,et al. Two subtypes of HIV-1 among injection-drug users in southern China[J]. Lancet,1998,351(9111):1250. |
| [21] Cheng HH,Zhang JP,Capizzi J,et al. HIV-1 subtype E in Yunnan,China[J]. Lancet,1994,344(8927):953-954. |
| [22] Xing H,Liang H, Wan ZY,et al. Distribution of recombinant human immunodeficiency virus type-1 CRF01_AE strains in China and its sequence variations in the env V3-C3 region[J]. Chin J Prev Med,2004,38(5):300-304. (in Chinese) 邢辉,梁浩,万卓越,等. 中国CRF01_AE亚型人类免疫缺陷病毒毒株的分子流行病学研究[J]. 中华预防医学杂志,2004,38(5):300-304. |
 2015, Vol. 36
2015, Vol. 36