文章信息
- 傅煜, 雷渊才, 曾伟生
- Fu Yu, Lei Yuancai, Zeng Weisheng
- 区域尺度杉木生物量估计的不确定性度量
- Uncertainty Assessment in Regional-Scale Above Ground Biomass Estimation of Chinese Fir
- 林业科学, 2014, 50(12): 79-86
- Scientia Silvae Sinicae, 2014, 50(12): 79-86.
- DOI: 10.11707/j.1001-7488.20141211
-
文章历史
- 收稿日期:2014-01-22
- 修回日期:2014-06-30
-
作者相关文章
2. 国家林业局调查规划设计院 北京 100714
2. Academy of Forest Inventory and Planning, State Forestry Administration Beijing 100714
森林生物量、碳储量及森林固碳能力是评价全球大气碳收支的重要参数(李海奎等,2010)。森林碳储量和固碳能力主要的计算基础是森林生物量,因此,国内外已在国家及区域尺度上开展了大量基于森林资源清查数据的森林生物量和碳储量估算研究(Lehtonen et al.,2007; McRoberts et al.,2014; 李海奎等,2010)。基于森林资源清查数据的大尺度森林生物量和碳储量估算一般采用系统抽样方法进行样地布设,样地内立木生物量估计以单木异速生长模型(包含树干、树枝、树叶和树根)为基础,合计得到样地水平生物量,再通过样地加权平均等方式推算林分及更大尺度范围的森林生物量。
从单木水平到样地水平再到区域水平,不确定性普遍存在于生物量估测的各个阶段(Cohen et al.,2013)。例如用调查数据推算单木生物量时,不确定性的主要来源是自变量的测量误差和异速生长模型的估测误差(Chave et al.,2004; Zianis,2005),其中测量误差受测量条件、技术、设备及人为等因素影响(McRoberts,1996; Lessard et al.,2001; Berger et al.,2014),而模型估计和预测误差主要包括模型函数形式定义不当(Breidenbach et al.,2014)、模型残差变异(Cunia,1987; Lessard et al.,2001; McRoberts et al.,2014)和模型参数误差(Ståhl et al.,2011)等。引起以上误差的原因可能是缺少模型校正数据或缺乏建模技术(Berger et al.,2014)、建模样本不足和待估数据超出自变量的有效区间(Chave et al.,2004)、树种及立地条件与特定的异速生长模型不匹配等。在从单木生物量推算到样地、林分及更大尺度生物量时,不确定性主要来源于抽样误差和单木水平生物量外推时传播并累积下来的误差,其中抽样误差是受样地数量、样地大小、抽样方式及自然条件等因素影响的结果,区域水平生物量估计及误差传递过程见图 1(Chave et al.,2004)。因此,基于森林资源清查数据的生物量估计在由单木水平、样地水平推算到区域水平的过程中存在大量不确定性或抽样和模型误差,忽略这些不确定性或误差将导致高估或低估区域尺度生物量的估测结果(Dietze et al.,2008)。
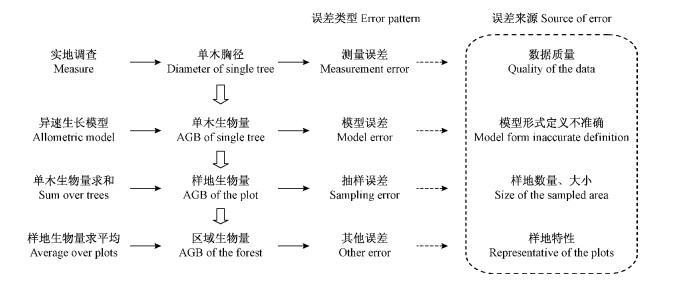 |
图 1 固定样地生物量估测中误差传递的形式及误差来源 Fig. 1 Form and source of error propagation in biomass estimation of permanent sample plot |
《联合国气候变化框架公约》(UNFCCC)下的政府间气候变化专门委员会(IPCC)指南明确提出,所有缔约国均有义务按照可监测、可汇报、可核查的“三可”原则(MRV)报告本国森林生物量、碳储量和碳汇能力的估计,以及生物量和碳储量估计中不确定性的测量方法、度量结果及降低措施(Penman et al.,2000; Eggleston et al.,2006)。此外,森林地上生物量是IPCC认定的、符合“三可”原则的5种森林碳库之一,提交精准的地上生物量和不确定性或误差估计结果,不仅对将来的国家温室气体排放报告至关重要,而且对促成地面数据和致力于监测局部、区域和全球尺度下的森林生物量和土地覆盖变化的遥感技术精准对接具有重大意义(Cohen et al.,2013)。目前,国外在森林生物量不确定性度量及精度分析等方面有一些研究(Keller et al.,2001; Lehtonen et al.,2007; Chave et al.,2004; Cohen et al.,2013),但国内在该领域研究还比较滞后(王仲锋,2006),现有文献很少考虑森林生物量不确定性的估测与度量,特别是用森林资源连续清查数据估计区域水平的森林生物量时,仅计算总随机误差,没有按误差来源分别度量。鉴于不同来源的不确定性相对于生物量估计值的占有率大小存在较大差异(Peltoniemi et al.,2006),因此分别度量有利于分析森林生物量估计效率和精度,对基于森林资源连续清查数据估计生物量和度量生物量不确定性或误差在理论上很有意义,实践上更具有价值。
测量误差、模型误差和抽样误差代表了生物量估计和预测中主要的误差来源或不确定性,不确定性的度量通常以标准误或均方根误差为表达形式(Chave et al.,2004; Ahmed et al.,2013)。生物量估计中不确定性的度量主要有3种方法。第1种方法是结合抽样理论的模型分析法,该方法在系统抽样理论基础上,以泰勒级数原理,经一系列数学变换和处理,可以分别度量抽样误差和模型误差导致的生物量估计的不确定性。结合抽样理论的模型分析法较早由Cunia(1987)、Gertner等(1992)应用于区域森林蓄积量估测的不确定性度量,最近有Ståhl等(2011)、Gregoire等(2010)、Gobakken等(2012)、Nelson等(2012)、Ene等(2012)应用于激光遥感数据估计生物量的不确定性。第2种方法是误差传递法,该方法通过建立误差随时间或空间累积的函数关系来度量不确定性,较早被广泛应用于估测多元数学模型自变量的随机误差。Gertner(1987; 1990)曾将误差传递法应用于蓄积估测中的误差度量,证明该方法在大大节省工作量及计算时间的同时,估测精度与蒙特卡洛法不相上下。但误差传递法较易受抽样误差和模型误差自相关的影响,且以抽样、模型、测量误差以及由测量误差引起的模型拟合偏差机械相加的形式表达估测总误差是不够严谨的。第3种方法是蒙特卡洛模拟法(McRoberts,1996; Lessard et al.,2001),该方法是在详细设定的误差水平下,通过反复模拟生物量估测过程来获得模型参数误差的概率分布(Peltoniemi et al.,2006),目前应用较广泛,但只考虑了模型误差,度量过程中需要不断假设不同的误差水平,计算过程复杂且计算量非常大(McRoberts et al.,2014)。
考虑到估计生物量基础数据和目前广泛使用的生物量估计方法,本文以第7次全国森林资源连续清查系统抽样体系江西省调查数据中的南方主要树种杉木(Cunninghamia lanceolata)为生物量估测对象,应用结合抽样理论的模型分析法,采用广泛使用的异速生长模型建立杉木地上生物量及其各组分生物量模型,以均方根误差为不确定性度量指标,测算估计抽样和模型误差引起的生物量不确定性以及各种不确定性相对比率(由于清查体系无法提供可用于度量测量误差的观测数据,本文暂不考虑),为准确度量生物量估计误差或不确定性、提高我国森林生物量估计水平和预报精度提供技术方法和思路。
1 数据来源本研究数据来源于第7次全国森林资源连续清查系统抽样体系江西省固定样地数据,以南方主要树种杉木为研究对象。江西省固定样地数为2 610个,每个样地面积为0.067 hm2,有林样地1 673个,起测直径均为5 cm,包括29个树种139 783株树,其中杉木占全树种数的40.7%。杉木调查数据的单木胸径统计情况见表 1。
|
|
建立杉木地上生物量模型和各组分生物量模型所用数据为我国南方杉木的立木地上生物量实测数据,采集时间为2009年6—9月,其中杉木数据来自江西省70株样木。样木数按2,4,6,8,12,16,20,26,32,38 cm以上共10个径阶均匀分配,每个径阶的样木数按树高级从低到高也尽量均匀分配,在大尺度范围内具有广泛的代表性。全部样木都实测胸径、地径和冠幅,将样木伐倒后,测量其树干长度(树高)和活树冠长度(冠长),分干材、干皮、树枝、树叶称鲜质量,并分别抽取样品带回实验室,在85 ℃恒温下烘干至恒重,根据样品鲜质量和干质量分别推算出样木各部分干质量并汇总得到地上部分干质量。由于江西省森林资源连续清查数据中没有包括树高实测数据,因此本文仅采用胸径为唯一自变量分别建立一元单木生物量和各组分生物量估测模型,建模数据统计情况见表 2。
|
|
本文采用结合抽样理论的模型分析法度量区域尺度生物量估测中的抽样误差和模型误差导致的不确定性,方法原理如下。
2.1 结合抽样理论的模型分析法原理假设S1,S2为2个独立样区,样区内各样地均为系统抽样布设,S1提供样区内每木调查数据,S2提供用于拟合单木生物量模型的建模数据,样本大小为M株。单木生物量模型为 $ Y\left(x \right)= \bar g\left({x,\alpha,\varepsilon } \right)$ ,其中x,α,ε分别为自变量、估计参数和随机误差对应的向量。S2生物量均值为 $ {{\bar \mu }_Y} = \frac{1}{M}\sum\limits_{i = 1}^M {\bar g\left({{x_{i2}},\alpha,{\varepsilon _{i2}}} \right)} $ ,当样本量足够大且参数α无偏时,该均值为:
| $ {\mu _Y} = \frac{1}{M}\sum\limits_{i = 1}^M g \left( {{x_{i2}},\alpha } \right)。 $ | (1) |
式中:x的下标2表示数据选自S2样本,i=1,…,M,μY可视为真实值。
对S1采用简单随机抽样的方式抽取m株样木,使用 $ Y\left(x \right)= \bar g\left({x,\alpha,\varepsilon } \right)$ 形式的生物量模型估测每木生物量及样区均值:
| $ {{\hat \mu }_Y} = \frac{1}{m}\sum\limits_{i = 1}^m g \left( {{x_{i1}},\hat \alpha } \right)。 $ | (2) |
式中: x的下标1表示数据选自S1样本,i=1,…,m, $ {\hat \alpha }$ 是α的无偏估计, $ {{\hat \mu }_Y}$ 可视为样本预测值(下文加^符号均表示预测变量)。样本预测值与真实值的离差是:
| $ \begin{array}{l} {{\hat \mu }_Y} - {\mu _Y} = \frac{1}{m}\sum\limits_{i = 1}^m g \left( {{x_{i1}},\hat \alpha } \right) - {\mu _Y} = \\ \left[ {\frac{1}{m}\sum\limits_{i = 1}^m g \left( {{x_{i1}},\alpha } \right) - {\mu _Y}} \right] + \\ \left\{ {\frac{1}{m}\sum\limits_{i = 1}^m {\left[ {g\left( {{x_{i1}},\hat \alpha } \right){\rm{ - }}g\left( {{x_{i2}},\alpha } \right)} \right]} } \right\}{\rm{ = }}\\ \left[ {\frac{1}{m}\sum\limits_{i = 1}^m g \left( {{x_{i1}},\alpha } \right){\rm{ - }}\frac{1}{M}\sum\limits_{i = 1}^M g \left( {{x_{i2}},\alpha } \right)} \right]{\rm{ + }}\\ \left\{ {\frac{1}{m}\sum\limits_{i = 1}^m {\left[ {g\left( {{x_{i1}},\hat \alpha } \right){\rm{ - }}g\left( {{x_{i1}},\alpha } \right)} \right]} } \right\}{\rm{ = }}\\ {D_1} + {D_2}。 \end{array} $ | (3) |
式中: $ {D_1} = \frac{1}{m}\sum\limits_{i = 1}^m {\bar g\left({{x_{i2}},\alpha } \right)} - \frac{1}{M}\sum\limits_{i = 1}^M {g\left({{x_{i2}},\alpha } \right)},{D_2} = \frac{1}{m}\sum\limits_{i = 1}^m {\left[ {g\left({{x_{i1}},\hat \alpha } \right)- g\left({{x_{i1}},\alpha } \right)} \right]} $ ,D1呈现了相同模型参数(均为α)不同样本(xi1和xi2)下离差,即该离差的随机性仅由样本量不同造成; 而D2呈现了不同模型参数( $ \hat \alpha \;$ 和α)相同样本(均为xi1)下离差,即该离差的随机性仅受模型参数不同的影响。由于D1,D2的随机性分别由S1,S2决定,S1,S2相互独立,因此D1,D2相互独立,且有E( $ {{\hat \mu }_Y}$ )=μY,那么 $ {{\hat \mu }_Y}$ 的方差有Var( $ {{\hat \mu }_Y}$ -μY)=Var(D1)+Var(D2)。假设测量数据准确无误,那么Var(D1)可表示抽样误差,Var(D2)可表示模型估测误差。目前对生物量估测中的误差度量通常统一归为一个抽样随机总误差Var( $ {{\hat \mu }_Y}$ -μY),没有将模型误差Var(D2)从总误差中分离出来。式(3)的推导和一些变化把总误差分离为抽样误差和模型误差2项,考虑到S1,S2来自于总体S,依据Ståhl等(2011)总误差估计式: $ Var\left({{{\hat \mu }_Y}} \right)= \frac{1}{m}\sigma _g^2 + g' \cdot {\mathop{\rm cov}} \left({\hat \alpha,\alpha } \right)\cdot {\left({g'} \right)^T}$ ,其中σg2为S的总体方差,g′为模型g对参数α的偏导,cov( $ \hat \alpha \;$ ,α)为参数的协方差阵。
2.2 单木总生物量及各组分生物量模型建立立木生物量模型的建立包括模型结构的选择和参数估计方法的确定2部分(曾伟生,2011)。本研究中单木地上总生物量及各组分生物量模型采用最简单也最常用的幂函数形式g=a(DBH)b+ε(Ter-Mikaelian et al.,1997),式中g为单木总生物量或各组分生物量,DBH为胸径,a,b为模型参数,ε为误差项。基于表 2提供的70株杉木建模数据,采用标准的最小二乘估计法进行非线性回归估计,分别拟合单木总生物量或各组分生物量模型相应的参数a,b。
2.3 泰勒级数在抽样估计中的原理基于江西省调查总体,全省包含系统布设连清固定样地n个,采用表 1数据和2.2节建立的单木总生物量和各组分生物量模型估计全省单木水平生物量值g(x, $ \hat \alpha \;$ ),合计各样地内单木生物量值预测样地水平生物量 $ {{\hat G}_j}$ ,公式为:
| $ {{\hat G}_j} = {{\hat G}_j}\left( {x,\hat \alpha } \right) = \sum\limits_i^{{n_j}} {g\left( {{x_{ij}},\hat \alpha } \right)} 。 $ | (4) |
式中: j为样地序号,j=1,…,n; i为单木号,i=1,…,nj,nj为第j号样地内样木株数。为了将模型估测误差从抽样误差中分离出来,本文取泰勒级数一阶展开项对式(4)进行线性化处理。泰勒级数展开式是对函数进行近似计算的有效方法,展开公式为:
| $ {{\hat G}_j}\left( {x,\hat \alpha } \right) \approx {G_j}\left( {x,a} \right) + {G_j}'\left( {\hat \alpha - \alpha } \right)。 $ | (5) |
式中: $ {G_j}' = \frac{{\partial G\left({x,\alpha } \right)}}{{\partial {\alpha _j}}},{G_j}\left({x,\alpha } \right)$ 中参数α可反映最近似真实值的模型参数。那么样地的单位面积生物量预测值为:
| $ \begin{array}{l} {{\hat R}_S} = \frac{{{{\hat G}_j}\left( {x,\hat \alpha } \right)}}{{{H_j}}} \approx \frac{{{G_j}\left( {x,\alpha } \right)}}{{{H_j}}} + \frac{{\left( {{G_j}'} \right) \cdot \left( {\hat \alpha - \alpha } \right)}}{{{H_j}}} = \\ \;\;\;\;\;\;\frac{{{G_j}\left( {x,\alpha } \right)}}{{{H_j}}} + C \cdot \left( {\hat \alpha - \alpha } \right)。 \end{array} $ | (6) |
式中: $ C = \frac{{{G_j}'}}{{{H_j}}}$ ,Hj为第j号样地面积。
2.4 抽样不确定性与模型估测不确定性度量假设RS为生物量总体真实值,可用全省生物量平均值表示,即 $ {{\tilde R}_S} = \frac{{\sum\limits_{j = 1}^n {{{\tilde G}_j}} \left({x,a,\varepsilon } \right)}}{{\sum\limits_{j = 1}^n {{H_j}} }},{{\tilde R}_S}$ 为RS的无偏估计,当样本量足够大时有E( $ {{\tilde R}_S}$ )≈E( $ {{\tilde R}_S}$ )≈RS= $ \frac{{\sum\limits_{j = 1}^n {{G_j}} \left({x,a} \right)}}{{\sum\limits_{j = 1}^n {{H_j}} }}$ 。那么生物量预测值 $ {{\hat R}_S}$ 的均方误差为:
| $ \begin{array}{l} E{\left( {{{\hat R}_S} - {R_S}} \right)^2} = \\ E{\left( {\frac{{{G_j}\left( {x,\alpha } \right)}}{{{H_j}}} - {R_S}} \right)^{\rm{2}}} + {\left[ {C \cdot \left( {\hat \alpha - \alpha } \right)} \right]^{\rm{2}}}{\rm{ + }}\\ {\rm{2}} \cdot E\left( {\frac{{{G_j}\left( {x,\alpha } \right)}}{{{H_j}}} - {R_S}} \right)\left[ {C \cdot \left( {\hat \alpha - \alpha } \right)} \right]。 \end{array} $ | (7) |
式中:第1项为样地生物量偏离全省生物量均值(即总体真值)的均方误差(MSES)。在不考虑测量及其他误差且假设模型近似效果良好的情况下,该误差的随机性仅由样本量不同决定,因此式(7)第1项反映的是抽样误差,变形后公式为:
| $ MS{E_s} = E{\left( {\frac{{{G_j}\left( {x,a} \right)}}{{{H_j}}} - {R_S}} \right)^2} = \frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}}。 $ | (8) |
式中: μH为样地面积Hj的平均值; σU2为样地与总体均值间离差(Uj=Gj-RS·Hj)的方差,有 $ \sigma _S^2 = \frac{{\sum\limits_{j = 1}^n {{{\left[ {{G_j}\left({x,a} \right)- {R_S} \cdot {H_j}} \right]}^2}} }}{{n - 1}}$
式(7)第2项为不同参数 $ {\hat \alpha }$ 偏离真值无偏参数α的均方误差。同理,该误差的随机性仅由模型决定,因此该项反映的是模型估测误差(MSEM),变换后公式为:
| $ MS{E_M} = E{\left[ {C \cdot \left( {\hat \alpha - \alpha } \right)} \right]^2} = C\sum {{C^T}。} $ | (9) |
式中: Σ为参数 $ {\hat \alpha }$ 的协方差矩阵cov( $ {\hat \alpha }$ ,α)。
式(7)第3项为样地生物量与全省生物量均值的离差平均值,显然 $ E\left[ {\frac{{{G_j}\left({x,\alpha } \right)}}{{{H_j}}} - {R_S}} \right] = 0$ ,式(7)第3项为零。因此(7)最终表达式为:
| $ E{\left( {{{\tilde R}_S} - {R_S}} \right)^2} = MS{E_S} + MS{E_M}{\rm{ = }}\frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}} + C\sum {{C^T}。} $ | (10) |
假设抽样误差和模型估测误差相互独立,那么生物量估测的总误差公式(Chave et al.,2004)为:
| $ MS{E_T} = MS{E_S} + MS{E_M}。 $ | (11) |
通常广泛采用均方根误差(RMSE)和相对均方根误差(Relative RMSE)表示生物量估测的不确定性,不确定性的度量指标表达如下。
总不确定性(RMSET和Relative RMSET):
| $ \begin{array}{l} RMS{E_T} = \sqrt {\frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}} + C\sum {{C^T}} } ;\\ {\mathop{\rm Re}\nolimits} lative\;\;\;\;RMS{E_T} = \sqrt {\frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}} + C\sum {{C^T}} } \cdot \frac{1}{{{R_S}}} \cdot 100\% 。 \end{array} $ | (12) |
抽样不确定性(RMSES和Relative RMSES):
| $ \begin{array}{l} RMS{E_T} = \sqrt {MS{E_S}} = \sqrt {\frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}}} ;\\ {\mathop{\rm Re}\nolimits} lative\;\;\;\;RMS{E_T} = \sqrt {MS{E_S}} = \\ \sqrt {\frac{1}{n} \cdot \frac{{\sigma _U^2}}{{\mu _H^2}}} \cdot \frac{1}{{{R_S}}} \cdot 100\% 。 \end{array} $ | (13) |
模型估测不确定性(RMSEM和Relative RMSEM):
| $ \begin{array}{l} RMS{E_M} = \sqrt {C\sum {{C^T}} } ;\\ {\mathop{\rm Re}\nolimits} lative\;\;\;\;RMS{E_T} = \sqrt {C\sum {{C^T}} } \cdot \frac{1}{{{R_S}}} \cdot 100\% 。 \end{array} $ | (14) |
本文单木地上生物量和各组分生物量估测模型利用R软件的nls()函数进行非线性回归,拟合模型参数a,b和决定系数(R2),估计单位面积生物量( $ {{\hat R}_S}$ )及参数协方差矩阵(Σ),并在此基础上推算均方根误差(RMSE)、相对均方根误差(Relative RMSE)和误差占有率(薛毅等,2007)。
3 结果与分析 3.1 单木生物量模型参数估计与参数协方差矩阵杉木地上部分总生物量模型和单木各组分生物量模型的参数估计见表 3。建模结果显示杉木单木地上生物量估计模型决定系数R2较高,为0.975,说明胸径对单木地上生物量的解释能力很强,其中胸径对树干(0.969)、树皮生物量(0.969)的解释能力也明显高于树枝(0.738)、树叶生物量(0.709)。
|
|
表 4为式(14)中模型参数协方差矩阵(Σ),估计结果是用于计算模型估测不确定性RMSEM的主要参数。由表 4可知,模型参数a和b呈负相关。
|
|
依据式(6),(12),(13),(14),以表 2、表 3和表 4中地上生物量数据,在不考虑测量误差情况下,表 5为第7次全国森林资源连续清查江西省杉木的地上生物量、不确定性、相对均方根误差和模型误差占有率。由表 5可知,江西省杉木地上生物量为19.34 t·hm-2,不确定性为0.92 t·hm-2,不确定性占杉木地上生物量的4.74%,其中由模型误差导致的不确定性为0.48 t·hm-2,占地上生物量的2.48%。杉木的模型估测误差占总误差约27%,即抽样误差对地上生物量估测精度的影响较大。
|
|
由表 2、表 3和表 4中各组分(即树干、树皮、树枝和树叶)生物量数据,依据式(6)和(14),在不考虑测量误差的情况下,第7次全国森林资源连续清查江西省杉木的各组分生物量和模型相对均方根误差见表 6和图 2。由表 6可知,杉木树干、树皮、树枝和树叶生物量分别为11.87,1.95,3.15,2.62 t·hm-2,其中由模型误差导致的不确定性分别占相应组分生物量的3.67%,3.43%,7.27%和6.33%。图 2显示,杉木树干、树皮生物量因模型估测误差导致的不确定性明显高于树枝、树叶,说明树枝和树叶的生物量估测模型拟合效果相对于树干和树皮较低,模型误差较大。
|
|
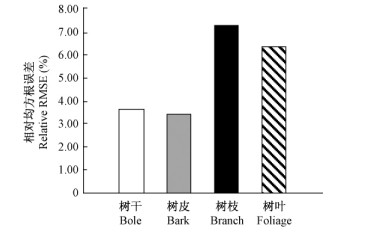 |
图 2 杉木各组分生物量模型相对均方根误差 Fig. 2 Relative RMSE of tree components due to model parameters |
杉木生物量估计的不确定性 约占生物量的5%,其中抽样误差对估计结果的影响大于模型估测误差,该结论与Breidenbach等(2014)基于挪威国家森林资源清查数据、McRoberts等(2014)基于美国森林资源调查数据和Berger等(2014)基于单木水平生物量估计的研究结论一致。但相对于现有研究,本文的模型估测误差占有率仍然过高(20%~30%)。原因可能有2点: 第一,抽样误差偏小。Ståhl等(2011)研究显示,抽样误差与样地大小密切相关。本文样地数据来自江西省系统布设样地,样木数据为样地内每木测量而非随机抽取,一定程度上降低了随机误差对抽样结果的影响,因此抽样误差相对总误差的占有率相应减少。第二,模型估测误差偏大。首先,由式(9)和(14)可知,测算模型估测误差导致的不确定性有赖于生物量模型参数的协方差阵( Σ)。本文杉木的建模数据70株,用于推算全省上万株林木的模型估测误差,建模数据量可能偏小,从而导致模型不确定性的度量结果偏大。该结论与Zianis等(2005)和Ståhl等(2011)一致。其次,本文建模数据的立地条件、起源、年龄分布与覆盖全省系统抽样样地中的林木差异较大也可能是导致模型估测误差偏大的原因,本文没有按照立地条件、起源、年龄分别建模和讨论。最后,由于残差变异性与生物量模型的估计精度直接相关,因残差引起的模型误差可通过蒙特卡洛模拟法进行测算,该部分研究不在本文讨论范围内。因此,增加建模数据样本量、考虑不同立地条件、增加解释变量个数等方式可能是提高生物量模型估计精度、降低模型估测不确定性的有效途径; 此外,由残差变异性导致的模型估测误差或不确定性也有待进一步研究。
各组分生物量估计中,树干和树皮的生物量模型拟合效果优于树枝和树叶,原因主要为胸径对树干和树皮生物量的解释能力明显强于树枝、树叶。此外,由于树枝、树叶更新快,枯死组织多,数据采集难度大等特点,相应的生物量模型拟合效果会较差,从而导致模型不确定性远高于树干、树皮。本文没有对地下部分生物量估计(例如树根)的不确定性进行度量,由于胸径对树根生物量的解释能力可能也不高,相应的模型不确定性很可能也非常高(Repola,2008; 2009; Marklund,1988)。由于本文的研究重点在于探索不同误差来源对生物量估计不确定性的影响,因此本文没有考虑各组分生物量间的相容性问题,相关问题还有待进一步探索。
本研究方法的优势在于,适用于度量基于森林资源连续清查数据的生物量估计中的不确定性,同时,能把导致生物量估计不确定性的抽样误差和模型误差从总误差中分离出来,并能精确度量不确定性中的抽样误差和模型误差。由于碳储量只需在生物量值基础上乘以系数0.5,那么导致不确定性的误差来源及传播方式也与生物量类似,因此本文研究方法同样适用于碳储量估计中的不确定性度量。
| [1] |
李海奎,雷渊才.2010.中国森林植被生物量和碳储量评估.北京:中国林业出版社.( 2) 2)
|
| [2] |
王仲锋.2006.森林生物量建模与精度分析.北京:北京林业大学博士学位论文.( 1) 1)
|
| [3] |
薛毅,陈立萍.2007.统计建模与R软件.北京:清华大学出版社.( 1) 1)
|
| [4] |
曾伟生.2011.全国立木生物量方程建模方法研究.北京:中国林业科学研究院博士学位论文.( 1) 1)
|
| [5] |
Ahmed R,Siqueira P,Hensley S,et al. 2013.Uncertainty of forest biomass estimates in north temperate forests due to allometry: implications for remote sensing.Remote Sensing,5(6):3007-3036.( 1) 1)
|
| [6] |
Berger A,Gschwantner T,McRoberts R E,et al.2014.Effects of measurement errors on individual tree stem volume estimates for the Austrian national forest inventory.Forest Science,60(1): 14-24.( 3) 3)
|
| [7] |
Breidenbach J,Antón-Fernández C,Petersson H,et al. 2014.Quantifying the model-related variability of biomass stock and change estimates in the Norwegian national forest inventory.Forest Science,60(1):25-33.( 2) 2)
|
| [8] |
Chave J,Condit R,Aguilar S,et al. 2004.Error propagation and scaling for tropical forest biomass estimates.Philosophical Transactions of the Royal Society of London.Series B: Biological Sciences,359(1443):409-420.( 6) 6)
|
| [9] |
Cohen R,Kaino J,Okello J,et al. 2013.Propagating uncertainty to estimates of above-ground biomass for Kenyan mangroves: a scaling procedure from tree to landscape level.Forest Ecology and Management,310:968-982.( 3) 3)
|
| [10] |
Cunia T.1987.Error of forest inventory estimates: its main components.Estimating tree biomass regressions and their error.USDA For Serv Gen Tech Rep NE-117 303.( 2) 2)
|
| [11] |
Dietze M C,Wolosin M S,Clark J S.2008.Capturing diversity and interspecific variability in allometries: a hierarchical approach.Forest Ecology and Management,256(11):1939-1948.( 1) 1)
|
| [12] |
Eggleston S,Buendia L,Miwa K,et al. 2006.IPCC guidelines for national greenhouse gas inventories.Institute for Global Environmental Strategies,Hayama,Japan.( 1) 1)
|
| [13] |
Ene L T,Næsset E,Gobakken T,et al. 2012.Assessing the accuracy of regional LiDAR-based biomass estimation using a simulation approach.Remote Sensing of Environment,123:579-592.( 1) 1)
|
| [14] |
Gertner G.1987.Notes: approximating precision in simulation projections: an efficient alternative to Monte Carlo methods.Forest Science,33(1):230-239.( 1) 1)
|
| [15] |
Gertner G,Kohl M.1992.An assessment of some nonsampling errors in a national survey using an error budget.Forest Science,38(3):525-538.( 1) 1)
|
| [16] |
Gertner G Z.1990.The sensitivity of measurement error in stand volume estimation.Canadian Journal of Forest Research,20(6):800-804.( 1) 1)
|
| [17] |
Gobakken T,Næsset E,Nelson R,et al. 2012.Estimating biomass in Hedmark County,Norway using national forest inventory field plots and airborne laser scanning.Remote Sensing of Environment,123:443-456.( 1) 1)
|
| [18] |
Gregoire T G,Ståhl G,Næsset E,et al. 2010.Model-assisted estimation of biomass in a LiDAR sample survey in Hedmark county,Norway.Canadian Journal of Forest Research,41(1):83-95.( 1) 1)
|
| [19] | IPCC.2006.Guidelines for national greenhouse gas inventories.IGES,Japan. |
| [20] |
Keller M,Palace M,Hurtt G.2001.Biomass estimation in the Tapajos National Forest,Brazil: examination of sampling and allometric uncertainties.Forest Ecology and Management,154(3):371-382.( 1) 1)
|
| [21] |
Lehtonen A,Cienciala E,Tatarinov F,et al. 2007.Uncertainty estimation of biomass expansion factors for Norway spruce in the Czech Republic.Annals of Forest science,64(2):133-140.( 2) 2)
|
| [22] |
Lessard V C,McRoberts R E,Holdaway M R.2001.Diameter growth models using minnesota forest inventory and analysis data.Forest Science,47(3):301-310.( 3) 3)
|
| [23] |
Marklund L G.1988.Biomass functions for pine,spruce and birch in Sweden.Rapport-Sveriges Lantbruksuniversitet,Institutionen foer Skogstaxering.( 1) 1)
|
| [24] |
McRoberts R E.1996.Estimating variation in field crew estimates of site index.Canadian Journal of Forest Research,26(4):560-565.( 1) 1)
|
| [25] |
McRoberts R E,Westfall J A.2014.Effects of uncertainty in model predictions of individual tree volume on large area volume estimates.Forest Science,60(1):34-42.( 4) 4)
|
| [26] |
Nelson R,Gobakken T,Naesset E,et al. 2012.Lidar sampling-using an airborne profiler to estimate forest biomass in Hedmark County,Norway.Remote Sensing of Environment,123:563-578.( 1) 1)
|
| [27] |
Peltoniemi M,Palosuo T,Monni S,et al. 2006.Factors affecting the uncertainty of sinks and stocks of carbon in Finnish forests soils and vegetation.Forest Ecology and Management,232(1):75-85.( 2) 2)
|
| [28] |
Penman J,Kruger D,Galbally I,et al. 2000.Good practice guidance and uncertainty management in national greenhouse gas inventories.IPCC National Greenhouse Cost Inventories programme,Technical Support Unit.( 1) 1)
|
| [29] |
Repola J.2008.Biomass equations for birch in Finland.Silva Fennica,42(4):605-624.( 1) 1)
|
| [30] |
Repola J.2009.Biomass equations for Scots pine and Norway spruce in Finland.Silva Fennica,43(4):625-647.( 1) 1)
|
| [31] |
Ståhl G,Holm S,Gregoire T G,et al. 2001.Model-based inference for biomass estimation in a LiDAR sample survey in Hedmark County,Norway.Canadian Journal of Forest Research,41: 96-107.( 5) 5)
|
| [32] |
Ter-Mikaelian M T,Korzukhin M D.1997.Biomass equations for sixty-five North American tree species.Forest Ecology and Management,97(1):1-24.( 1) 1)
|
| [33] |
Zianis D,Muukkonen P,MäkipääR,et al. 2005.Biomass and stem volume equations for tree species in Europe.Sliva Fennica Monorgraphs,(4):1-63.( 2) 2)
|
 2014, Vol. 50
2014, Vol. 50

