文章信息
- 董利虎, 李凤日, 贾炜玮
- Dong Lihu, Li Fengri, Jia Weiwei
- 东北林区天然白桦相容性生物量模型
- Compatible Tree Biomass Models for Natural White Birch (Betula platyphylla) in Northeast China Forest Area
- 林业科学, 2013, 49(7): 75-85
- Scientia Silvae Sinicae, 2013, 49(7): 75-85.
- DOI: 10.11707/j.1001-7488.20130711
-
文章历史
- 收稿日期:2012-10-09
- 修回日期:2013-04-26
-
作者相关文章
森林生物量是森林生态系统最基本的数量特征,既可表明森林的经营水平和开发利用价值,又能反映森林与其环境在物质循环和能量流动上的复杂关系,特别是森林生物量在减小温室效益、稳定调节全球碳平衡与碳循环、评价森林循环贡献和固碳能力方面具有不可替代的作用(Caldeira et al.,2000 ;Fang et al.,2001 ; 王效科等,2001 ; Houghton,2005 ; Muukkonen,2006 ; Woodbury et al.,2007)。目前测算森林生物量常用的方法为生物量模型估算法(Parresol,1999 ; 罗云建等,2009),它是利用林木易测因子来推算难以测定的立木生物量(特别是树根生物量)(方精云等,1996 ; 宇万太等,2001),可以减少测定生物量的外业工作。虽然在建模过程中需要测定一定数量的样木生物量,但建立生物量模型后,在同类林分中就可以利用森林资源清查资料来估计整个林分和单木的生物量; 特别是在大范围的森林生物量调查中,利用生物量模型能大大减少调查工作量。为了满足立木总生物量等于各分项生物量之和这一逻辑关系,需要各分项生物量模型之间具有可加性(相容性)。骆期邦等(1999)、张会儒等(1999)引入用线性联立模型和非线性联合估计模型来解决总量与各分项之间的相容性问题; 唐守正等(2000)以及胥辉等(2001)对不同非线性联合估计方案进行对比研究,并提出了2级联合估计的方法; Parresol(2001)提出采用非线性似乎不相关模型来解决非线性生物量方程的可加性问题; Bi等(2004)建立了以对数转换为基础的可加性生物量方程系统,并采用似乎不相关模型对方程参数和偏差校正因子进行联合估计。目前,利用非线性联立方程组模型来确保总生物量与各分量相容的研究已经有很多(Carvalho et al.,2003 ; Brandeis et al.,2006 ; Bi et al .,2010 ; 曾伟生等,2010 ; 董利虎等,2011 ; Li et al .,2013),与传统模型相比,联立方程组模型不仅能一定程度上提高模型的精度,而且还解决了总生物量与各分项生物量的相容性问题。
白桦(Betula platyphylla)是我国东北地区分布范围较广、所占比重较大的森林类型。白桦用途广泛,价值昂贵,其资源受到越来越多的重视。目前,我国研究白桦相容性生物量模型的报道还较少。本文以天然白桦生物量实测数据为基础,利用非线性度量误差联立方程组估计的方法,采用2种方案来建立天然白桦一元和二元相容性生物量模型,为区域及国家尺度上森林生态系统生物量和碳储量的估算提供依据。
1 数据与方法 1.1 数据来源本文所用的2011年天然白桦林22块标准地主要分布于黑龙江省大兴安岭(塔河县和新林林业局)、小兴安岭(黑河市和五营林业局)以及长白山地区(宁安市、五常市和三岔子林业局)。由于天然白桦林的林龄很难确定,因此本文选择树种组成和立地质量类似的地块作为天然白桦的标准地。每个标准地的大小为0.06 hm2,对每个标准地都进行每木检尺。每个标准地根据胸径大小选取白桦优势木、中等木和被压木各1株作为解析木。解析木需在样地外选取,选取原则为解析木胸径与优势木、中等木和被压木胸径大小的误差不超过± 5 % 。将选好的解析木伐倒,树高超过15 m 按2 m 区分段,树高低于15 m 按1 m 区分段,测定各区分段树干的鲜质量。将树冠分为3层,每层选取3~5个标准枝称其枝叶的鲜质量。每株解析木各区分段的树干和每层的枝叶都分别取样。由于小根(直径 < 5 mm)对根系总生物量的影响不大且全部挖掘出来非常困难,所以只对直径大于5 mm 的树根进行挖掘(Wang,2006),分别测定大根(> 5 cm)、粗根(2~5 cm)、细根(< 2 cm)的鲜质量,并分别取样品。所采集样品带回室内在105 ℃烘干至恒重,测定其含水量,计算出各分项干质量比,进而得出解析木的生物量。
本文天然白桦解析木为66株,为了更好地建模以及对模型进行检验,将数据按照3:1分为建模数据与检验数据,建模数据与检验数据随机筛选,其生物量统计量见表 1 。
|
|
建立相容性立木生物量模型的目的是为了以后进行更好的预估,所以在模型中尽可能选择和生物量关系密切并在立木中容易获取的测树因子,而胸径和树高容易获取且具有一定的准确性。基于以上条件,本文选择相对生长方程(CAR)模型形式作为总量和各分项基础模型,模型分为一元生物量模型和二元生物量模型,其形式如下:
| $ {{w}_{i}}={{a}_{i}}{{D}^{{{b}_{i}}}}; $ | (1) |
| $ {{w}_{i}}={{a}_{i}}{{({{D}^{2}}H)}^{{{b}_{i}}}}。 $ | (2) |
式中:wi为生物量;D为胸径;H为树高;ai,bi为待估计的模型参数,i= 1~7,分别代表总生物量、地上部分、树根、树干、树枝、树叶和树冠。
天然白桦总生物量及各分项生物量采用式(1),(2)分别拟合,然后从相容性的定义出发,构造总生物量与各分项生物量的相容性生物量模型。本文采用2种方案来建立天然白桦一元和二元相容性立木生物量模型。
1.2.1 以总生物量为基础分级控制方案1)天然白桦一元相容性立木生物量模型 参照唐守正等(2000)提出的思路,以总生物量为基础,采用三级控制的方法进行相容性立木生物量模型的建立: 一级控制变量为总生物量,将所有树种总生物量的独立模型进行回归估计,通过一级控制按比例分配使地上部分生物量和树根生物量之和等于总生物量;二级控制变量为地上部分生物量,通过二级控制按比例分配使地上部分生物量等于树干生物量和树冠生物量之和; 三级控制变量为树冠生物量,通过三级控制按比例分配使树冠生物量等于树枝生物量和树叶生物量之和。
一级控制:
| $ \begin{align} & {{{\hat{w}}}_{2}}=\frac{{{f}_{2}}\left(x \right)}{{{f}_{2}}\left(x \right)+{{f}_{3}}\left(x \right)}\times {{{\hat{w}}}_{1}},\ & {{{\hat{w}}}_{3}}=\frac{{{f}_{3}}\left(x \right)}{{{f}_{2}}\left(x \right)+{{f}_{3}}\left(x \right)}\times {{{\hat{w}}}_{1}},\ \end{align}; $ | (3) |
二级控制:
| $ \begin{align} & {{{\hat{w}}}_{4}}=\frac{{{f}_{4}}\left(x \right)}{{{f}_{4}}\left(x \right)+{{f}_{7}}\left(x \right)}\times {{{\hat{w}}}_{2}},\ & {{{\hat{w}}}_{2}}=\frac{{{f}_{7}}\left(x \right)}{{{f}_{4}}\left(x \right)+{{f}_{7}}\left(x \right)}\times {{{\hat{w}}}_{2}}; \ \end{align} $ | (4) |
三级控制:
| $ \begin{align} & {{{\hat{w}}}_{5}}=\frac{{{f}_{5}}\left(x \right)}{{{f}_{5}}\left(x \right)+{{f}_{6}}\left(x \right)}\times {{{\hat{w}}}_{7}},\ & {{{\hat{w}}}_{6}}=\frac{{{f}_{6}}\left(x \right)}{{{f}_{5}}\left(x \right)+{{f}_{6}}\left(x \right)}\times {{{\hat{w}}}_{7}}。 \ \end{align} $ | (5) |
式中: f2(x),f3(x),f4(x),f5(x),f6(x)和f7(x)分别为各树种地上部分、地下部分(树根)、树干、树枝、树叶、树冠生物量的基础模型;${{{\hat{w}}}_{1}}$为总生物量的估计值;${{{\hat{w}}}_{i}}$为联合估计后的估计值,i为2~7,分别代表地上部分、树根、树干、树枝、树叶和树冠。
一级控制: 首先对式w1 = a1Db1进行基础模型的拟合,得到总生物量模型的参数和估计值${{{\hat{w}}}_{1}}$,将${{{\hat{w}}}_{1}}$直接代入式(3),可组成如下方程组:
| $ {{{\hat{w}}}_{2}}=\frac{{{a}_{2}}{{D}^{{{b}_{2}}}}}{{{a}_{2}}{{D}^{{{b}_{2}}}}+{{a}_{3}}{{D}^{{{b}_{3}}}}}{{{\hat{w}}}_{1}}=\frac{1}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{1}}; $ | (6) |
| $ {{{\hat{w}}}_{3}}=\frac{{{a}_{2}}{{D}^{{{b}_{2}}}}}{{{a}_{2}}{{D}^{{{b}_{2}}}}+{{a}_{3}}{{D}^{{{b}_{3}}}}}{{{\hat{w}}}_{1}}=\frac{{{r}_{1}}{{D}^{{{r}_{2}}}}}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{1}}。 $ | (7) |
式中:${{{\hat{w}}}_{1}}$为总生物量的估计值,${{{\hat{w}}}_{2}}$,${{{\hat{w}}}_{3}}$为联合估计后的地上部分生物量、树根生物量估计值。
对式(6),(7)进行参数简化,$\frac{{{\alpha }_{3}}}{{{\alpha }_{2}}}={{r}_{1}}$,b3-b2 =r2,其中,a2,b2 为地上部分生物量模型参数,a3,b3 为树根生物量模型参数,它们都为联合估计待估参数,经过简化后得到r1和r2。r1和r2为联合估计待估参数,其初值为地上部分(树干、树冠生物量之和)、树根基础模型的参数估计值。
二级控制: 以${{{\hat{w}}}_{2}}$为基础,可组成如下方程组:
| $ {{{\hat{w}}}_{4}}=\frac{{{a}_{4}}{{D}^{{{b}_{4}}}}}{{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{7}}{{D}^{{{b}_{7}}}}}{{{\hat{w}}}_{2}}=\frac{1}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{2}}; $ | (8) |
| $ {{{\hat{w}}}_{7}}=\frac{{{a}_{7}}{{D}^{{{b}_{7}}}}}{{{a}_{7}}{{D}^{{{b}_{7}}}}+{{a}_{7}}{{D}^{{{b}_{7}}}}}{{{\hat{w}}}_{2}}=\frac{{{r}_{1}}{{D}^{{{r}_{2}}}}}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{2}}。 $ | (9) |
对式(8),(9)进行参数简化,$\frac{{{\alpha }_{7}}}{{{\alpha }_{4}}}={{r}_{1}}$,b7-b4 =r2,其中a4,a7,b4,b7 为联合估计待估参数(同理,a4,b4 为树干生物量模型参数; a7,b7 为树冠生物量模型参数),经过简化后得到r1和r2,r1和r2为联合估计待估参数,其初值为树冠(树枝和树叶生物量之和)、树干基础模型的参数估计值。
三级控制: 以${{{\hat{w}}}_{7}}$为基础,可组成如下方程组:
| $ {{{\hat{w}}}_{5}}=\frac{{{a}_{5}}{{D}^{{{b}_{5}}}}}{{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{{\hat{w}}}_{7}}=\frac{1}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{7}}; $ | (10) |
| $ {{{\hat{w}}}_{6}}=\frac{{{a}_{5}}{{D}^{{{b}_{5}}}}}{{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{{\hat{w}}}_{7}}=\frac{{{r}_{1}}{{D}^{{{r}_{2}}}}}{1+{{r}_{1}}{{D}^{{{r}_{2}}}}}{{{\hat{w}}}_{7}}。 $ | (11) |
式中:$\frac{{{\alpha }_{6}}}{{{\alpha }_{5}}}={{r}_{1}}$,b6 -b5 =r2,a5,a6,b5,b6 为联合估计待估参数(a5,b5 为树枝生物量模型参数; a6,b6 为树叶生物量模型参数),经过简化后得到r1和r2,r1和r2为联合估计待估参数,其初值为树枝、树叶基础模型的参数估计值。
2)天然白桦二元相容性立木生物量模型 首先对总生物量用式 w1 = a1(D2H)b1进行基础模型的拟合,得到总生物量模型的参数和估计值${{{\hat{w}}}_{1}}$,将式(6),(7),(8),(9),(10)和(11)中的D换为D2H,得出二元相容性立木生物量模型。
1.2.2 以总生物量为基础直接控制方案1)天然白桦一元相容性立木生物量模型 天然白桦一元相容性立木生物量模型构建形式如下:
| $ \left\{ \begin{matrix} \begin{matrix} {{w}_{3}}={{a}_{3}}{{D}^{{{b}_{3}}}}, \\ {{w}_{4}}={{a}_{4}}{{D}^{{{b}_{4}}}}, \\ \end{matrix} \\ {{w}_{5}}={{a}_{5}}{{D}^{{{b}_{5}}}}, \\ \begin{matrix} {{w}_{6}}={{a}_{6}}{{D}^{{{b}_{6}}}}, \\ {{w}_{1}}={{a}_{1}}{{D}^{{{b}_{1}}}}={{a}_{3}}{{D}^{{{b}_{3}}}}+{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}。 \\ \end{matrix} \\ \end{matrix} \right. $ | (12) |
式中:w1,w3,w4,w5和w6 分别表示总生物量、树根、树干、树枝和树叶; a1,a3,a4,a5,b1,b3,b4,b5和b6 是其模型的参数。式(12)为以总生物量为基础直接控制模型,其能确保总生物量 = 树干 + 树枝 +树叶 + 树根,满足总生物量与各分项生物量的相容。
由式(12)推出:
| $ \left\{ \begin{matrix} \begin{matrix} \begin{matrix} \begin{matrix} {{w}_{3}}=\frac{{{a}_{3}}{{D}^{{{b}_{3}}}}}{{{a}_{3}}{{D}^{{{b}_{3}}}}+{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}= \\ \frac{{{r}_{3}}{{D}^{{{k}_{3}}}}}{1+{{r}_{1}}{{D}^{{{k}_{1}}}}+{{r}_{2}}{{D}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{{{k}_{3}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}; \\ \end{matrix} \\ {{w}_{4}}=\frac{{{a}_{4}}{{D}^{{{b}_{4}}}}}{{{a}_{3}}{{D}^{{{b}_{3}}}}+{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}= \\ \end{matrix} \\ \begin{matrix} \frac{1}{1+{{r}_{1}}{{D}^{{{k}_{1}}}}+{{r}_{2}}{{D}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{{{k}_{3}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}; \\ {{w}_{5}}=\frac{{{a}_{5}}{{D}^{{{b}_{5}}}}}{{{a}_{3}}{{D}^{{{b}_{3}}}}+{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}= \\ \end{matrix} \\ \end{matrix} \\ \frac{{{r}_{1}}{{D}^{{{k}_{1}}}}}{1+{{r}_{1}}{{D}^{{{k}_{1}}}}+{{r}_{2}}{{D}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{{{k}_{3}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}; \\ {{w}_{6}}=\frac{{{a}_{6}}{{D}^{{{b}_{6}}}}}{{{a}_{3}}{{D}^{{{b}_{3}}}}+{{a}_{4}}{{D}^{{{b}_{4}}}}+{{a}_{5}}{{D}^{{{b}_{5}}}}+{{a}_{6}}{{D}^{{{b}_{6}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}= \\ \frac{{{r}_{2}}{{D}^{{{k}_{2}}}}}{1+{{r}_{1}}{{D}^{{{k}_{1}}}}+{{r}_{2}}{{D}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{{{k}_{3}}}}}{{a}_{1}}{{D}^{{{b}_{1}}}}。 \\ \end{matrix} \right. $ | (13) |
式中:r1 = a5 /a4 ;r2 = a6 /a4 ;r3= a3 /a4 ;k1= b5 -b4 ;k2= b6 -b4 ;k3= b3 -b4 。
式(13)为以总生物量为基础直接控制方案一元相容性立木生物量模型形式,r1,r2,r3,r4,k1,k2,k3,k4,a1,b1为联合估计待估参数,其初值为总生物量、树干、树枝、树叶和树根基础模型的参数估计值。
2)天然白桦二元相容性立木生物量模型 对于式(13),将D换成 D2H,就为二元相容性立木生物量模型的化简式,记为式(14):
| $ \left\{ \begin{matrix} \begin{matrix} \begin{matrix} \begin{matrix} \begin{matrix} {{w}_{3}}={{a}_{1}}{{r}_{3}}{{D}^{2{{k}_{3}}+2{{b}_{1}}}}{{H}^{{{k}_{3}}+{{b}_{1}}}}/(1+{{r}_{1}}{{D}^{2{{k}_{1}}}}{{H}^{{{k}_{1}}}}+ \\ {{r}_{2}}{{D}^{2{{k}_{2}}}}{{H}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{2{{k}_{3}}}}{{H}^{{{k}_{3}}}}); \\ \end{matrix} \\ {{w}_{4}}={{a}_{1}}{{D}^{2{{b}_{1}}}}{{H}^{{{b}_{1}}}}/(1+{{r}_{1}}{{D}^{2{{k}_{1}}}}{{H}^{{{k}_{1}}}}+{{r}_{2}}{{D}^{2{{k}_{2}}}}{{H}^{{{k}_{2}}}}+ \\ \end{matrix} \\ {{r}_{3}}{{D}^{2{{k}_{3}}}}{{H}^{{{k}_{3}}}}) \\ \end{matrix} \\ {{w}_{5}}={{a}_{1}}{{r}_{1}}{{D}^{2{{k}_{1}}+2{{b}_{1}}}}{{H}^{{{k}_{1}}+{{b}_{1}}}}/(1+{{r}_{1}}{{D}^{2{{k}_{1}}}}{{H}^{{{k}_{1}}}}+ \\ \end{matrix} \\ {{r}_{2}}{{D}^{2{{k}_{2}}}}{{H}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{2{{k}_{3}}}}{{H}^{{{k}_{3}}}}); \\ {{w}_{6}}={{a}_{1}}{{r}_{2}}{{D}^{2{{k}_{1}}+2{{b}_{1}}}}{{H}^{{{k}_{1}}+{{b}_{1}}}}/(1+{{r}_{1}}{{D}^{2{{k}_{1}}}}{{H}^{{{k}_{1}}}}+ \\ {{r}_{2}}{{D}^{2{{k}_{2}}}}{{H}^{{{k}_{2}}}}+{{r}_{3}}{{D}^{2{{k}_{3}}}}{{H}^{{{k}_{3}}}})。 \\ \end{matrix} \right. $ | (14) |
当自变量和因变量的观测值中都含有度量误差,使得通常回归模型方法不再适用时,需采用度量误差模型方法(Tang et al.,2001 ; 2002 ; 唐守正等,2008)。本文在建立白桦总生物量与各分项生物量模型时,直径(D)和树高(H)是可以选定的精确观测的量,认为它是无误差变量(外生变量)。生物量观测值的误差来自2方面: 观测误差和随机抽样误差。生物量观测值是状态变量(内生变量),因此可以用非线性度量误差模型进行参数估计。本文采用 ForStat 2.1中的非线性度量误差联立方程组模块进行计算。
另外,生物量模型普遍存在异方差性,本文生物量模型也不例外,因此必须选用适当的权函数来进行加权回归估计或者采用将模型化为对数模型以消除异方差。对数转换能有效地解决异方差现象,但对数转换会产生偏差,故需采用校正系数CF$[CF=EXP\left(\frac{\text{MSE}}{2} \right)]$校正后获得总生物量无偏估计值(Baskerville,1972 ; 曾伟生等,2011 a)。目前在加权回归方面已经有了许多成果(曾伟生等,1999;胥辉,1999 ; Saint-André et al.,2005 ; Vallet et al.,2006),研究表明,在进行加权回归时所用的权函数是针对某一个模型,并不对任何一类模型都是适宜的。所以,本文对幂函数这种简单形式的模型采用对数转换的方式进行异方差的消除,对于复杂的相容性模型采用加权回归的方法来消除异方差。本文权函数的选取方法为: 用各分项基础模型拟合产生残差的方差来建立自变量为胸径的回归方程g(x),则权函数为G= 1/g(x),即权重变量为G= 1/Dx。在采用 ForStat 2.1软件对参数进行求解时,在每一个方程两边同乘以权重变量G=1/Dx。
1.2.4 模型的评价指标本文采用以下6个指标对模型拟合和检验进行评价: 确定系数(R2)、均方误差(MSE)、模拟效率(EF)、平均相对误差(ME,%)、平均相对误差绝对值(MAE,%)和预测精度(P,%),具体定义见文献(李凤日,2004 ; 曾伟生等,2011 b)。
2 结果与分析 2.1 以总生物量为基础分级控制方案(方案1)相容性立木生物量模型拟合利用以总生物量为基础分级控制方案(方案1)建立天然白桦相容性立木生物量时,首先将w1 =a1(D)b1和w1 = a1(D2H)b1 转化为对数形式来消除总生物量模型的异方差,即将模型转变为lnw1 =r1+r2lnD和lnw1 = r1+r2ln(D2H)(其中: r1= lna1,r2 = lnb1),进而采用分级控制方法得出总生物量与各分项生物量模型的参数估计值以及模型的评价指标(表 2)。
|
|
由表 2可知,以总生物量为基础分级控制方案所建立的天然白桦总生物量与各分项生物量模型的确定系数(R2)均在0.80以上,均方误差 MSE 都较小。所建立的一元相容性生物量模型中,总生物量、树根、树干、树叶和树枝生物量模型的平均相对误差 ME 都在± 10 % 以内; 绝大多数模型的平均相对误差绝对值 MAE 在30 % 以内,只有树叶模型的 MAE 略高于30 % 。总体来说各分项及总生物量模型拟合程度较好。对于二元相容性生物量模型来说,绝大多数模型的平均相对误差均在± 10 % 内; 绝大多数模型的平均相对误差绝对值 MAE 均未超过30 %,其中树枝、树叶生物量模型的平均相对误差绝对值较大; 在一元、二元相容性生物量模型中,总生物量和树干生物量模型的模拟效率 EF 接近于1,树根、树枝和树叶冠的模拟效率相对较小,但也都在0.8以上; 总生物量和树干模型的预测精度P相对较高,树根、树枝和树叶的较低,但都在70 % 以上。总生物量选用对数模型不仅能很好地预估生物量,还能有效地消除总生物量模型的异方差(图 1 、图 3)。本文各分项所采用的加权回归方法不仅能改善模型的异方差现象,还能很好地估计天然白桦各部分生物量(图 2 、图 4)。总的来说,利用总生物量为基础分级控制方案所建立的一元、二元相容性生物量模型曲线与各样本点之间具有较好的切合程度,所建立的相容性生物量模型能很好地对天然白桦生物量进行估计。
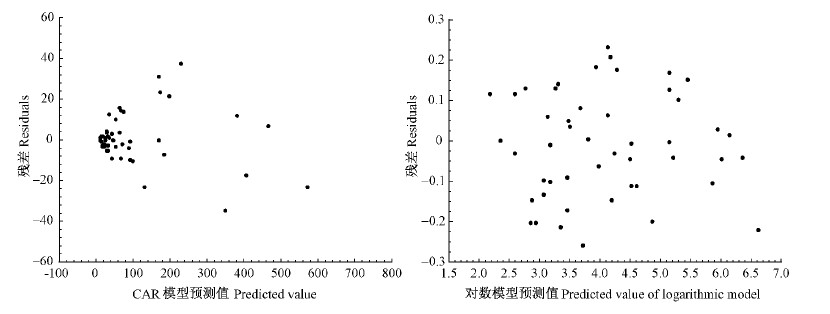 |
图 1 方案1天然白桦一元总生物量模型残差
Fig. 1 Residuals of mono-element total biomass models of program 1 for natural white birch
|
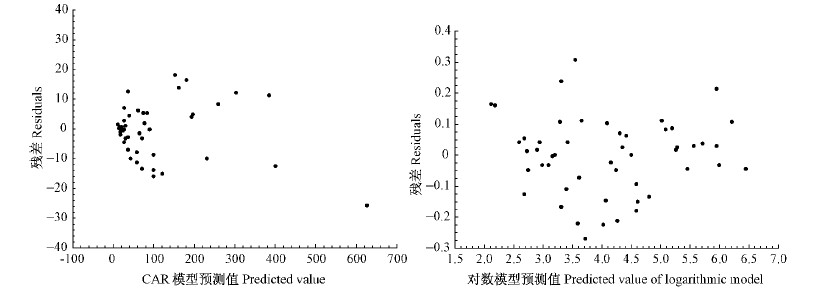 |
图 3 方案1天然白桦二元总生物量模型残差
Fig. 3 Residuals of dual-element total biomass models of program 1 for natural white birch
|
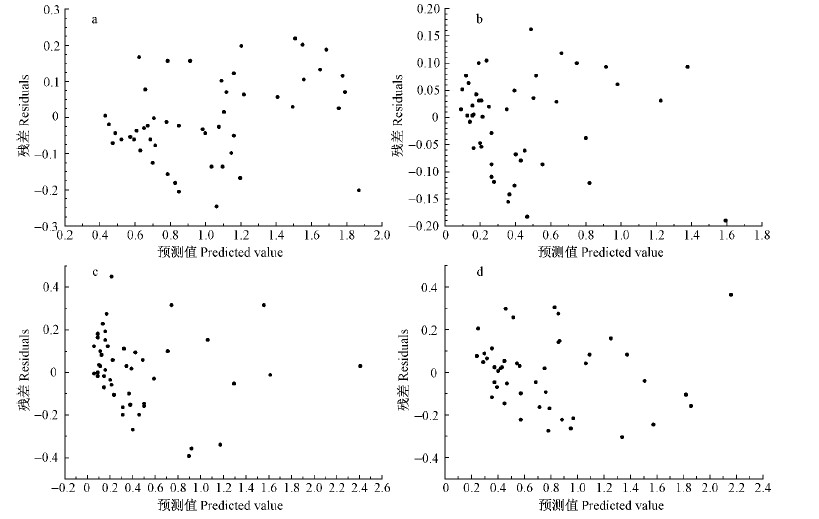 |
图 2 方案1天然白桦各分项一元相容性生物量模型消除异方差后残差
Fig. 2 Residuals of mono-element compatible tree biomass models of program 1 for natural white birch after eliminating heteroscedasticity
a.树干 Stem; b.树枝 Branch; c.树叶 Foliage; d.树根 Root. |
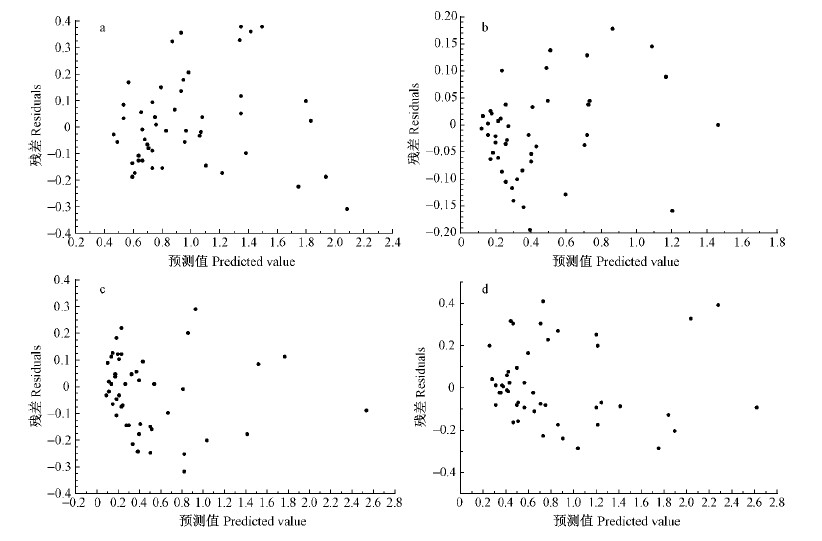 |
图 4 方案1天然白桦各分项二元相容性生物量模型消除异方差后残差
Fig. 4 Residuals of dual-element compatible tree biomass models of program 1 for natural white birch after eliminating heteroscedasticity
a.树干 Stem; b.树枝 Branch; c.树叶 Foliage; d.树根 Root. |
从表 2可以看出,树根、树枝和树叶一元相容性生物量模型的评价指标都优于二元相容性生物量模型,而总生物量、树干二元相容性生物量模型的评价指标稍好于一元相容性生物量模型,即增加树高作为变量可以有效地提高总生物量和树干生物量的预测精度,这与许多研究一致(Cole et al.,2006 ;Wang,2006 ; António et al.,2007)。总的来说,2种模型类型的相容性生物量模型都能对天然白桦生物量进行很好的预估,以总生物量为基础分级控制方案所建立的一元相容性生物量模型优于二元相容性生物量模型。
2.2 以总生物量为基础直接控制方案(方案2)相容性立木生物量模型拟合利用以总生物量为基础直接控制方案(方案2)所建立的总生物量与各分项相容性生物量模型的参数估计值以及模型的评价指标见表 3 、表 4 。
|
|
|
|
由表 4可知,一元、二元相容性生物量模型的确定系数(R2)均在0.80以上,其中以总生物量和树干较大,树根、树叶和树枝较小,所有模型均方误差MSE 都较小; 绝大多数模型的平均相对误差 ME 在± 10 % 内,所建立模型的平均相对误差绝对值 MAE在11.1 %~33.8 % 之间; 总生物量和树干的模拟效率 EF 在0.90以上,树根、树枝和树叶的模拟效率相对较差,但也都在0.8以上; 总生物量和树干的预测精度P较高,都达到了90 % 以上,树根、树枝和树叶较低,但基本都在70 % 以上。利用加权回归方法对模型进行异方差的改善和消除,效果也很明显(图 5~8)。总之,2种模型类型的相容性生物量模型曲线与各样本点之间具有较好的切合程度,模型具有一定的预估性。
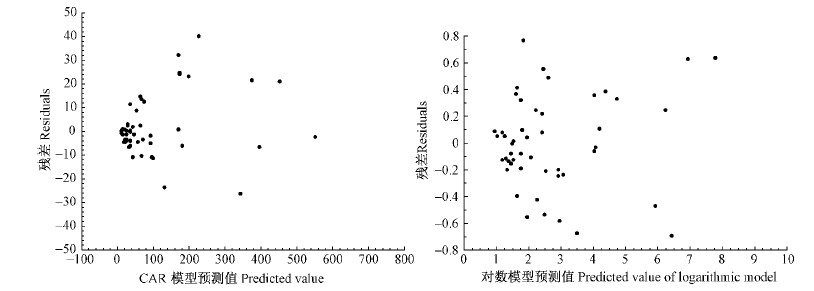 |
图 5 方案2天然白桦一元总生物量模型残差
Fig. 5 Residuals of mono-element total biomass models of program 2 for natural white birch
|
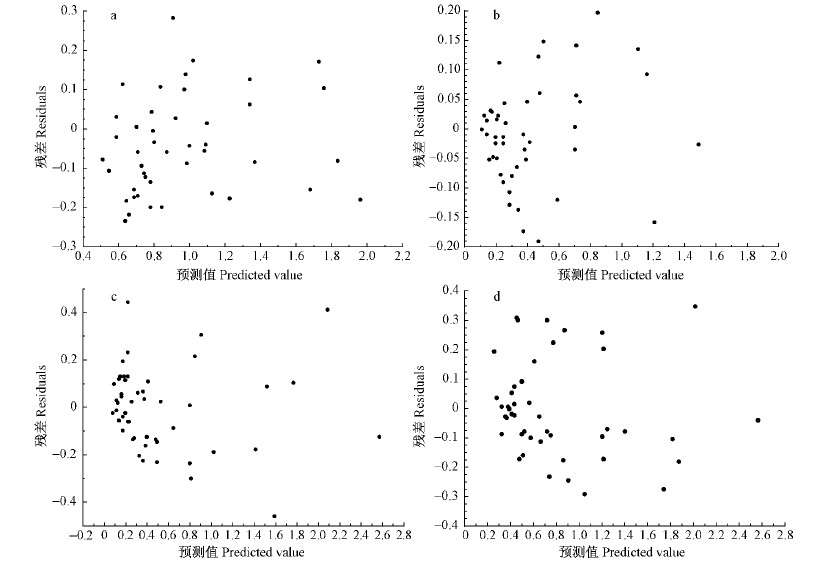 |
图 6 方案2天然白桦各分项一元相容性生物量模型消除异方差后残差
Fig. 6 Residuals of mono-element compatible tree biomass models of program 2 for natural white birch after eliminating heteroscedasticity
a.树干 Stem; b.树枝 Branch; c.树叶 Foliage; d.树根 Root. |
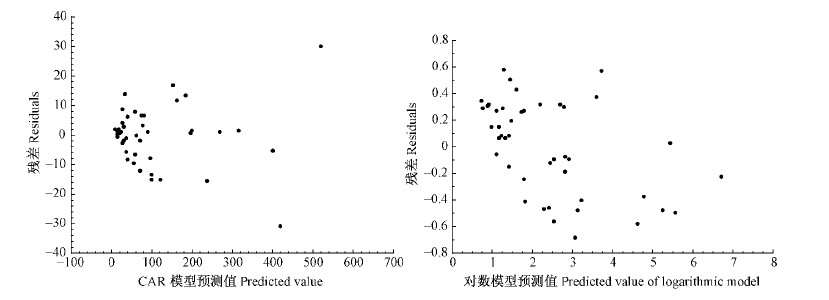 |
图 7 方案2天然白桦二元总生物量模型残差
Fig. 7 Residuals of dual-element total biomass models of program 2 for natural white birch
|
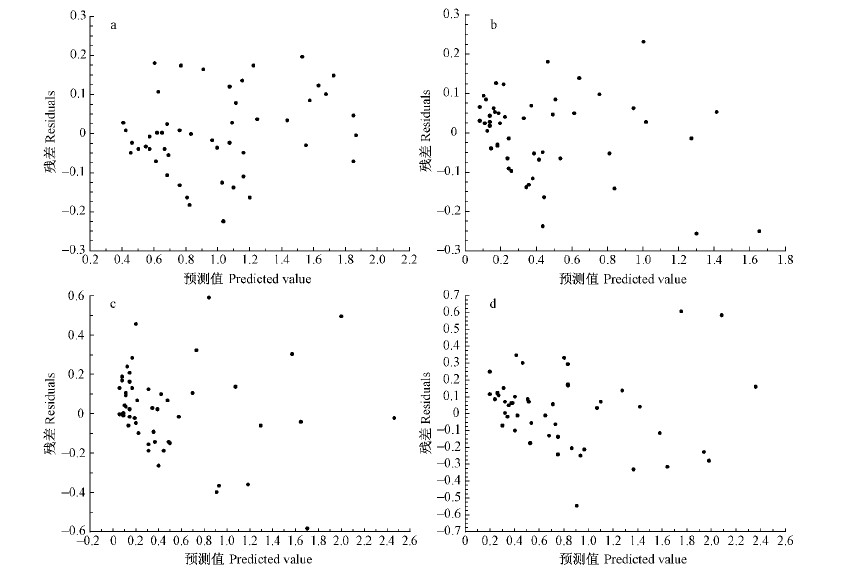 |
图 8 方案2天然白桦各分项二元相容性生物量模型消除异方差后残差
Fig. 8 Residuals of dual-element compatible tree biomass models of program 2 for natural white birch after eliminating heteroscedasticity
a.树干 Stem; b.树枝 Branch; c.树叶 Foliage; d.树根 Root. |
利用以总生物量为基础直接控制方案建立的天然白桦相容性立木生物量模型中,树根、树枝和树叶一元相容性生物量模型的评价指标优于二元相容性生物量模型,总生物量和树干二元相容性生物量模型的模型评价指标略好于一元相容性生物量模型。 2种形式的相容性生物量模型都能对天然白桦生物量进行很好的预估。总的来说,以总生物量为基础直接控制方案所建立的一元相容性生物量模型优于二元相容性生物量模型。
2.3 天然白桦不同方案相容性生物量模型比较结合表 2和表 4,对2种方案的一元相容性立木生物量模型进行对比 : 以总生物量为基础直接控制方案建立的总生物量、树干、树枝和树叶模型的相关系数 R2高于以总生物量为基础分级控制方案建立的生物量模型 ; 均方误差方面 : 以总生物量为基础直接控制方案好于以总生物量为基础分级控制方案 ; 2种方案的模拟效率差异不大 ; 以总生物量为基础直接控制方案建立的绝大多数模型的平均相对误差ME、平均相对误差绝对值MAE以及预测精度P都优于以总生物量为控制分级控制方案。从模型的构造及应用性来说,以总生物量为基础直接控制方案所建立的一元相容性立木生物量模型优于以总生物量为基础分级控制方案所建立的一元相容性立木生物量模型。同理,对于2种方案的二元相容性立木生物量模型来说,以总生物量为基础直接控制方案略好于以总生物量为基础分级控制方案。
3 结论与讨论本文采用2种方案,利用非线性度量误差联立方程组的方法建立了天然白桦一元、二元相容性立木生物量模型,并采用对数转换和加权回归的方法进行异方差的消除。结果表明: 2种方案都能解决总生物量与各分项生物量的相容性问题; 2种方案所建立的天然白桦一元、二元相容性生物量模型的确定系数R2都在0. 8以上,模拟效率EF在0.8以上; 2种方案中绝大多数总生物量与各分项生物量模型的平均相对误差和平均相对误差绝对值在± 10 %和± 30 % 内,总体来说各分项生物量和总生物量模型的拟合效果较好; 2种方案所建立的相容性生物量模型的预测精度基本都在80 % 以上,树枝和树叶生物量模型的预测精度较差,但也在69 % 以上。本文所建立的相容性生物量模型中,总生物量和树干生物量模型效果较好,树根、树叶和树枝生物量模型效果较差,可能是由于白桦树梢经常分叉或者抽样误差的存在使数据变动范围变大影响了模型拟合和估计的效果。这与 Wang(2006)对中国东北地区10个温带树种、董利虎等(2011)对黑龙江主要树种、 Li等(2013)对中国南方杉木(Cunninghamia lanceolata)生物量模型的研究结果一致。
许多研究表明,在生物量模型中加入树高(H)能提高立木生物量模型的精度(Cole et al.,2006 ;Wang,2006 ; António et al.,2007),Wang(2006)和Zhou等(2007)研究显示树高是预测树干、树枝、树叶生物量的重要变量。本文研究表明,一元相容性生物量模型好于二元相容性生物量模型,以总生物量为基础直接控制方案所建立的一元和二元相容性立木生物量模型好于以总生物量为基础分级控制方案所建立的相容性生物量模型。主要原因是总生物量与树干生物量与胸径(D)和树高(H)的关系都非常密切(Wang,2006 ; António et al.,2007),而树枝、树叶和树根生物量只与胸径关系密切,与树高关系不是很密切,在其生物量模型中加入树高(H)在一定程度上可能降低了模型的精度,所以2种方案建立的一元相容性生物量模型好于二元相容性生物量模型。另外,以总生物量为基础分级控制方案会使每级产生的误差叠加,所以以总生物量为基础直接控制方案建立的相容性生物量模型效果更好。总的来说,2种方案所建立的相容性生物量模型都具有一定精度,都能对天然白桦生物量进行很好的预估,但考虑到模型形式的复杂程度,在进行生物量预估时,建议采用以总生物量为基础直接控制方案建立相容性生物量模型。
为了提高生物量模型的精度,以后应在外业进行枝解析时应尽量避免树枝、树叶部分生物量的损失。在实地进行调查时,应选取各个径阶的样木,这样建立的模型具有一定的适用性。本文白桦样木主要集中在中小径阶,在样木大小选取方面有所欠缺。
本文数据来源于3个地区共66株解析木,所建立的生物量模型存在着估计尺度的问题。考虑样本数的局限性,本文所建立的生物量模型更适合应用于东北林区天然白桦的生物量估算。本文建立了一元和二元相容性生物量模型,对于省级行政区域等大尺度的生物量估计而言,采用一元模型可能是最为合适的; 而对于某些小尺度的生物量估计,采用二元模型进行生物量估计可能会更为准确。
| [1] |
董利虎,李凤日,贾炜玮,等. 2011.含度量误差的黑龙江省主要树种生物量相容性模型. 应用生态学报, 22 (10): 2653-2661.( 2) 2)
|
| [2] |
方精云,刘国华,徐崇玲. 1996. 我国森林植被的生物量和净生产量.生态学报, 16 (5): 497-508.( 1) 1)
|
| [3] |
李凤日. 2004. 长白落叶松人工林树冠形状的模拟. 林业科学, 40 (5): 16-24.( 1) 1)
|
| [4] |
骆期邦,曾伟生,贺东北,等. 1999. 立木地上部分生物量模型的建立及其应用研究. 自然资源学报,14 (3): 271-277.( 1) 1)
|
| [5] |
罗云建,张小全,王效科,等. 2009. 森林生物量的估算方法及其研究进展. 林业科学, 45 (8): 129-134.( 1) 1)
|
| [6] |
唐守正,张会儒,胥辉. 2000. 相容性生物量模型的建立及其估计方法研究. 林业科学, 36 (专刊1): 19-27.( 2) 2)
|
| [7] |
唐守正,郎奎建,李海奎. 2008. 统计和生物数学模型计算(ForStat教程). 北京: 科学出版社.( 1) 1)
|
| [8] |
王效科,冯宗炜. 2001. 中国森林生态系统的植物碳储量和碳密度研究. 应用生态学报, 12 (1): 13-16.( 1) 1)
|
| [9] |
胥辉,刘伟平. 2001. 相容性生物量模型研究. 福建林学院学报, 21 (1): 18-23.( 1) 1)
|
| [10] |
胥辉. 1999. 生物量模型方差非齐性研究. 西北林学院学报, 19 (2): 73-77.( 1) 1)
|
| [11] |
宇万太,于永强. 2001. 植物地下生物量研究进展. 应用生态学报, 12 (6): 927-932.( 1) 1)
|
| [12] |
张会儒,赵有贤,王学力,等. 1999. 应用线性联立方程组方法建立相容性生物量模型研究. 林业资源管理, (6): 93-96.( 1) 1)
|
| [13] |
曾伟生,骆期邦,贺东北. 1999. 论加权回归与建模. 林业科学, 35 (5): 5-11.( 1) 1)
|
| [14] |
曾伟生,唐守正. 2010. 利用度量误差模型方法建立相容性立木生物量方程系统. 林业科学研究, 23 (6): 797-803.( 1) 1)
|
| [15] |
曾伟生,唐守正. 2011a. 非线性模型对数回归的偏差校正及与加权回归的对比分析. 林业科学研究, 24 (2): 137-143.( 1) 1)
|
| [16] |
曾伟生,唐守正. 2011b. 立木生物量模型的优度评价和精度分析. 林业科学, 47 (11): 106-113.( 1) 1)
|
| [17] |
António N A N, Tomé M T M, Tomé J T J, et al. 2007. Effect of tree, stand, and site variables on the allometry of Eucalyptus globulus tree biomass. Can J For Res, 37 (5): 895-906.( 3) 3)
|
| [18] |
Baskerville G L. 1972. Use of logarithmic regression in the estimation of plant biomass. Can J For Res, 2 (1): 49-53.( 1) 1)
|
| [19] |
Bi H, Turner J, Lambert M J. 2004. Additive biomass equations for native eucalypt forest trees of temperate Australia. Trees, 18 (4): 467-479.( 1) 1)
|
| [20] |
Bi H, Long Y, Turner J, et al. 2010. Additive prediction of aboveground biomass for Pinus radiata (D. Don)plantations. For Ecol Manage. 259 (12): 2301-2314.( 1) 1)
|
| [21] |
Brandeis T J, Delaney M, Parresol B R, et al. 2006. Development of equations for predicting Puerto Rican subtropical dry forest biomass and volume. For Ecol Manage, 233 (1): 133-142.( 1) 1)
|
| [22] |
Caldeira K, Duffy P B. 2000. The role of the southern ocean in uptake and storage of anthropogenic carbon dioxide. Science, 287 (5453): 620-622.( 1) 1)
|
| [23] |
Carvalho J P, Parresol B R. 2003. Additivity in tree biomass components of Pyrenean oak (Quercus pyrenaica Willd.). For Ecol Manage, 179 (1/3): 269-276.( 1) 1)
|
| [24] |
Cole T G, Ewel J J. 2006. Allometric equations for four valuable tropical tree species. For Ecol Manage, 229 (1/3): 351-360.( 2) 2)
|
| [25] |
Fang Z, Bailey R L. 2001. Nonlinear mixed effects modeling for Slash pine dominant height growth following intensive silvicultural treatments. Forest Science, 47 (3): 287-300.( 1) 1)
|
| [26] |
Houghton R A. 2005. Aboveground forest biomass and the global carbon balance. Global Change Biology, 1(6): 945-958.( 1) 1)
|
| [27] |
Li H K, Zhao P X. 2013. Improving the accuracy of tree-level aboveground biomass equations with height classification at a large regional scale. For Ecol Manage, 289: 153-163.( 1) 1)
|
| [28] |
Muukkonen P. 2006. Forest inventory-based large-scale forest biomass and carbon budget assessment: new enhanced methods and use of remote sensing for verification. Helsinki: Department of Geography, University of Helsinki.( 1) 1)
|
| [29] |
Parresol B R. 1999. Assessing tree and stand biomass: a review with examples and, critical comparisons. Forest Science, 45 (4): 573-593.( 1) 1)
|
| [30] |
Parresol B R. 2001. Additivity of nonlinear biomass equations. Can J For Res, 31 (5): 865-878.( 1) 1)
|
| [31] |
Saint-André L, M'Bou A T, Mabiala A, et al. 2005. Age-related equations for above-and below-ground biomass of a Eucalyptus hybrid in Congo. For Ecol Manage, 205 (1/3): 199-214.( 1) 1)
|
| [32] |
Tang S Z, Li Y, Wang Y H. 2001. Simultaneous equations, error-in-variable models and model integration in systems ecology. Ecol Model, 142 (3): 285-294.( 1) 1)
|
| [33] |
Tang S Z, Wang Y H. 2002. A parameter estimation program for the error-in-variable model. Ecol Model, 156 (2): 225-236.( 1) 1)
|
| [34] |
Vallet P, Dhôte J F, Le Moguédec G, et al. 2006. Development of total aboveground volume equations for seven important forest tree species in France. For. Ecol. Manage, 229 (1/3): 98-110.( 1) 1)
|
| [35] |
Wang C K. 2006. Biomass allometric equations for 10 co-occurring tree species in Chinese temperate forests. For Ecol Manage, 222 (1/3): 9-16.( 5) 5)
|
| [36] |
Woodbury P B, Smith J E, Heath L S. 2007. Carbon sequestration in the U.S.forest sector from 1990 to 2010. For Ecol Manage, 241 (1/3): 14-27.( 1) 1)
|
| [37] |
Zhou X, Brandle J R, Schoeneberger M M, et al. 2007. Developing above-ground woody biomass equations for open grown, multiple-stemmed tree species: Shelterbelt-grown Russian-olive. Ecol Model, 202 (3): 311-323.( 1) 1)
|
 2013, Vol. 49
2013, Vol. 49

