文章信息
- 黄永芳, 陈锡沐, 庄雪影, 雷治国, 陈永忠, 彭邵峰.
- Huang Yongfang, Chen Ximu, Zhuang Xueying, Lei Zhiguo, Chen Yongzhong, Peng Shaofeng.
- 油茶种质资源遗传多样性分析
- Analysis of Genetic Diversity in Camellia oleifera Germplasms
- 林业科学, 2006, 42(4): 38-43.
- Scientia Silvae Sinicae, 2006, 42(4): 38-43.
-
文章历史
- 收稿日期:2005-03-20
-
作者相关文章
2. 湖南省林业科学院 长沙 410004
2. Hunan Academy of Forestry Changsha 410004
油茶(Camellia oleifera)是一个适应性强、分布很广的树种, 具有重要的经济、社会和生态价值。油茶主要分布在我国南方17个省(区), 湖南、江西、广西、浙江和广东等为中心产区, 其中, 湖南省栽培面积最大, 约占全国油茶栽培面积的40%。我国油茶种质资源极为丰富, 各油茶产区都选育出了大量的优良单株、无性系和家系, 全国已选出180多个优良无性系, 其中, 湖南选出的优良无性系最多, 在生产上应用的已有100余个。无性系的形态特征受环境条件等因素的影响, 导致油茶分类的混乱, 同名异物、同物异名的现象经常发生, 迫切需要从分子水平上对油茶无性系进行研究。
目前我国油茶的研究主要限于栽培与常规育种, 着重进行传统的油茶良种选育和推广, 而对油茶分子生物学的研究较少, 仅对油茶DNA和RNA提取方法, 种子cDNA文库构建以及PCR条件的建立等进行了探讨(黄永芳等, 2004;胡芳名等, 2004;张智俊等, 2003), 陈永忠等(2005)对湘林3号等13个优良无性系作RAPD分子鉴别的探讨, 更多优良无性系的遗传多样性还没有深入的研究, 这严重影响了油茶这个具有重大经济价值树种的开发和利用。因此开展油茶分子水平的研究, 进行遗传多样性分析, 揭示油茶无性系间的亲缘关系, 可加快选育丰产、高产、抗病、优质的油茶品种。RAPD技术是Williams等(1990)和Welsh等(1990)发明的一种较为简便的检测DNA多态性技术, 能快速、简便而且准确地检测DNA的多态性。RAPD标记为显性标记, 尽管RAPD多态性谱带的重复性和稳定性较差, 但在分析种质资源亲缘关系和品种鉴别等方面还是非常有效的(罗军武等, 2000;梁月荣等, 2000;Fu, 2005;Ilbi, 2003;Koller et al., 1993;Park et al., 2002; Kaundun et al., 2002)。本文利用RAPD标记技术进行油茶遗传多样性分析, 并分析抗病性、产油量和果油率等农艺性状与分子标记的相关性, 分析油茶无性系间的亲缘关系, 为油茶优良种质资源的交流和科学利用提供参考, 并为RAPD技术在无性系的应用提供参考。
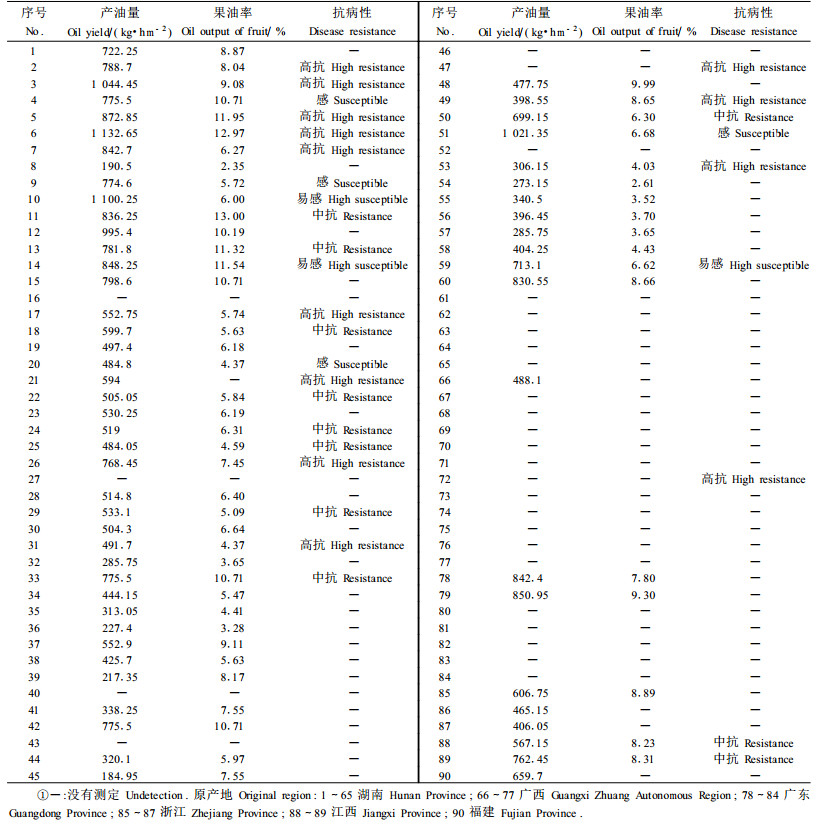
1 材料与方法 1.1 材料从湖南省林业科学院油茶种质资源基因库、广西岑溪软枝油茶种子园和华南农业大学林学院油茶种质资源圃采集90个无性系, 每个无性系选一植株采集嫩叶, 用硅胶快速干燥, 带回实验室用于分析。各无性系材料来源见表 1, 除了36、37、38、39、40、41、43、45、52、60号样品为寒露籽品种群外, 其他样品均为霜降籽品种群。60号是半同胞, 61~65号为杂交品种, 其余均为无性系。
|
|
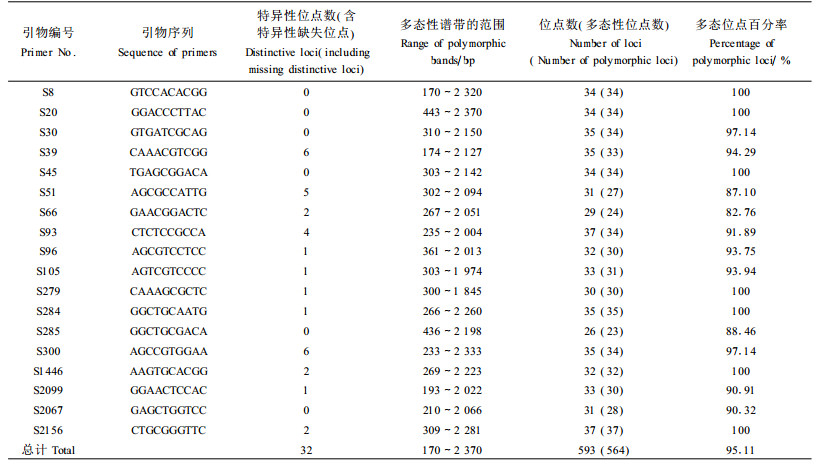
采用改进的CTAB法提取各油茶样品的总DNA。PCR扩增反应在PTC-100TM Peltier Thermal Cycler(MJ ResearchTM incorporated)上执行。采用20 μL反应体系:2 μL缓冲液, 20 ng模板DNA, 1.75 mmol·L-1 Mg2+, 0.1 mmol·L-1 dNTPs(上海生工生物工程有限公司), 1.0 U Taq酶(华美生物工程公司), 0.73 μmol·L-1引物(上海生工生物工程有限公司), 12.2 μL无菌水。采用优化后的扩增反应程序:95 ℃预变性3 min; 然后94 ℃变性1 min, 40 ℃退火1 min, 72 ℃延伸2 min, 40个循环; 最后72 ℃反应7 min。降至4 ℃后取出, 应用琼脂糖凝胶电泳检测(黄永芳等, 2004), 以100 bp DNA Ladder Plus(晶美生物工程有限公司)为分子量标准。从266个引物中筛选出18个条带清晰、多态性高、且可重复的引物。应用1.5%琼脂糖凝胶电泳检测扩增和模板DNA。
1.3 数据处理根据分子量标准的迁移率确定RAPD带的分子量。RAPD扩增谱带用“1"代表有, 用“0"代表无, 得到一个二元矩阵。将0-1矩阵在NTSYSpc(2.1版)软件中进行处理, 应用SIMQUAL(Similarity for Qualitative Data)法计算各无性系间遗传相似系数(F)和遗传距离(D)。用SAHN功能, 按照非加权两两对比法(UPGMA)进行聚类分析(Sokal et al., 1958)。Nei & Li遗传相似系数公式: F=2Nij/(Ni+Nj), 式中:Nij为材料i和j公共的条带数; Ni为材料i的总带数; Nj为材料j的总带数。遗传距离D=-lnF。根据相似系数构建聚类图。
对抗病性、产油量和果油率等农艺性状, 采用SAS 8.10软件, 进行与分子标记的相关性分析。通过接种炭疽病菌, 根据果实感病率, 把抗病性分为4个等级:1级, 高抗, 感病率0~3%;2级, 一般, 3% < 感病率≤5%;3级, 感病, 5% < 感病率≤10%;4级, 易感, 感病率>10%。产油量和果油率直接用该无性系在选种时测定的数据进行分析。产油量是指单位面积的茶油产量, 通过多年多点试验获得。果油率指茶油占鲜果的百分比, 先测定鲜果出籽率, 再测定鲜籽含水率, 然后测定干籽含油率, 最后换算成鲜果含油率即为果油率。
2 结果与分析 2.1 RAPD多态性用18条引物对90份样本进行了RAPD扩增, 共扩增出593条谱带, 每个引物扩增出23~37条带, 其中多态谱带564条, 多态位点百分率为95.11%。产生32条特异性和特异性缺失谱带, 占5.32%。扩增结果如表 2、图 1所示。
|
|
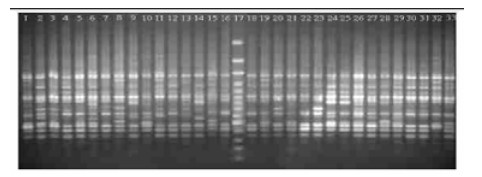
|
图 1 油茶总DNA随机扩增图谱(引物S1446) Fig. 1 RAPD profile using the template DNAof C. oleifera (by primer S1446) 第17泳道为Marker; 第1~16及第18~33泳道为样品RAPD扩增产物。 The 17th lane is Marker; Other lanes are RAPD patterns of C. oleifera. |
基于18条引物的RAPD扩增结果, 利用NTSYS-pc软件计算遗传相似系数。根据遗传相似系数进行油茶品种及无性系的聚类分析(图 2)。

|
图 2 由RAPD标记获得的油茶种质资源的UPGMA聚类 Fig. 2 Clustering of C. oleifera as determined by UPGMA from RAPD data |
供试的90个油茶无性系聚成了4类:第1类24个样本, 原产地都是湖南, 从已测定的产量结果看, 除了8号(产油量190.5 kg·hm-2), 其余的产油量都在750 kg·hm-2以上, 属于一个高产的类群; 第2类22个样本, 其中88号和89号原产地是江西, 86号和87号原产地是浙江, 它们和42号(原产地湖南)聚成一亚类; 第3类21个样本, 这类包括的区域较广, 有湖南、广西、广东、浙江和福建省区的油茶品种及无性系; 第4类23个样本, 这类中主要包括湖南、广西和广东3个省区的油茶品种及无性系, 其中广西的软枝油茶(74、75、76、77)和广东的阳春油茶(80、82、83、84)除了75之外(也在同一亚类), 全部聚类在一起, 同时产于湖南的5个半同胞(60、61、62、64和65)也聚到一个亚类中。
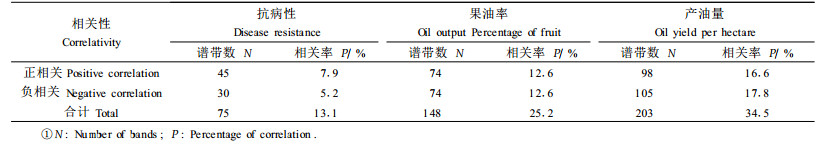
2.3 分子标记与农艺性状的相关性分析分别对抗病性、果油率和产油量与其对应扩增出来的谱带进行相关分析, 显著相关谱带结果统计于表 3。结果是75条谱带与抗病性显著相关, 占参与分析谱带572条的13.1%;148条谱带与果油率显著相关, 占参与分析谱带587条的25.2%;203条谱带与产油量显著相关, 占参与分析谱带589条的34.5%。
|
|
油茶属异花授粉植物, 自然异花授粉而形成的后代, 在形态、物候、生产力和抗病性等方面均表现出多样性, 由此自然产生很多类群和品种群。姜静等(2002)研究表明, 多态位点百分率可作为度量遗传变异水平高低的指标。本试验条件下RAPD扩增得到的593条谱带, 多态性谱带564条, 比例高达95.11%, 这表明油茶优良无性系遗传多样性相当丰富。油茶已有悠久的栽培历史, 可能在早期就有广泛的种内杂交现象发生, 这些油茶之间存在高度混合杂交的遗传现象。
广东阳春油茶和广西软枝油茶都是油茶的优良农家品种, 属霜降籽, 两者在果形、出籽率、含油率、产油量和抗性等数量性状方面都具有高度的相似性, 而且两者在植株的形态方面也有高度的一致性:植株分枝低, 主侧枝多而细, 分枝角度大, 枝条柔软等。从聚类分析结果来看, 广西软枝油茶和广东阳春油茶各4个无性系均聚在同一亚类, 因此, 从分子水平说明了阳春油茶和软枝油茶的亲缘关系比较近, 有可能是同一个农家品种。但两者在遗传距离上还是存在一定的差距, 可能是对环境适应的一种表现。
RAPD技术应用在品种、品系的分析鉴定中, 可以很好地反映各品种、品系的亲缘关系, 尤其在一些近缘品种、品系的分析鉴定中具有良好的应用前景(赵锦等, 2003;陈永忠等, 2005)。从本试验结果来看, RAPD扩增产生特异性谱带32条(包括特异性谱带19条和特异性缺失谱带13条)。可运用更多的引物来对这些油茶种质资源进行RAPD扩增, 寻找出更多的特异性谱带和特异性缺失谱带, 为油茶种质资源的鉴定和保护提供依据。
与抗病性、果油率和产油量等数量性状极显著相关谱带的确定, 可进行数量基因定位和基因转移, 加快选育高产、抗病的优质油茶品种, 缩短育种进程, 提高育种效率, 还能进一步为实现油茶良种化、区域化提供理论依据, 对油茶种质资源的保护和合理开发利用也具有重要的意义。本试验结果中有13.1%~34.5%的谱带与抗病性、果油率及产油量等农艺性状显著相关, 这些特异性谱带的确定还有待于进一步的研究。
陈永忠, 张智俊, 谭晓风. 2005. 油茶优良无性系的RAPD分子鉴别. 中南林学院学报, 25(4): 40-45. DOI:10.3969/j.issn.1673-923X.2005.04.009 |
胡芳名, 谭晓风, 石明旺, 等. 2004. 油茶种子cDNA文库的构建. 中南林学院学报, 24(5): 1-4. DOI:10.3969/j.issn.1673-923X.2004.05.001 |
黄永芳, 陈锡沐, 雷治国, 等. 2004. 油茶种质资源RAPD分析Ⅰ: DNA提取和PCR条件建立. 河南农业科学, (12): 22-25. DOI:10.3969/j.issn.1004-3268.2004.12.007 |
姜静, 杨传平, 刘桂丰, 等. 2002. 利用RAPD标记技术对桦树种间亲缘关系的分析. 林业科学, 38(1): 154-156. DOI:10.3321/j.issn:1001-7488.2002.01.025 |
梁月荣, 田中淳一, 武田善行. 2000. 茶树品种资源遗传多态性RAPD分析. 浙江林学院学报, 17(2): 215-218. DOI:10.3969/j.issn.2095-0756.2000.02.021 |
罗军武, 施兆鹏, 沈程文, 等. 2000. 茶树品种资源遗传亲缘关系的RAPD分析. 茶叶科学, (2): 140-146. |
张智俊, 谭晓风, 陈永忠. 2003. 同时提取油茶中DNA和RNA的简便方法. 生物技术, 13(3): 23-24. DOI:10.3969/j.issn.1004-311X.2003.03.015 |
赵锦, 刘孟军. 2003. 赞皇大枣优良品系及赞新大枣的RAPD分析. 林业科学, 39(3): 153-156. DOI:10.3321/j.issn:1001-7488.2003.03.025 |
Fu Yongbi. 2005. Geographic pattern of RAPD variation in cultivated flax. Crop Science, 45(3): 1084-1091. DOI:10.2135/cropsci2004.0345 |
Ilbi H. 2003. RAPD markers assisted varietal identification and genetic purity test in pepper, Capsicum annuum. Scientia Horticulturae, 97: 211-218. DOI:10.1016/S0304-4238(02)00158-9 |
Kaundun S S, Park Y G. 2002. Genetic structure of six Korean tea populations as revealed by RAPD-PCR markers. Crop Science, 42(2): 594-601. DOI:10.2135/cropsci2002.5940 |
Koller B, Lehmann A, MeDermott J M. 1993. Identification of apple cultivars using RAPD markers. Theor Appl Genet, 85: 901-904. |
Park Y G, Kaundun S S, Zhyvoloup A. 2002. Use of the bulked genomic DNA-based RAPD methodology to assess the genetic diversity among abandoned Korean tea plantations. Genetic Resources and Crop Evolution, 49(2): 159-165. DOI:10.1023/A:1014706528972 |
Sokal R R, Michener C D. 1958. A statistical method for evaluating systematic relationships. Univ Kansas Sci Bull, 38: 1409-1438. |
Welsh J, McClelland M. 1990. Fingerprinting genomes using PCR with arbitrary primers. Nucl Acids Res, 18: 7213-7218. DOI:10.1093/nar/18.24.7213 |
Williams J G K, Hanafey M K, Rubelik A R, et al. 1990. DNA polymorphisms amplified by arbitrary primers are useful as genetic markers. Nucl Acids Res, 18: 6231-6235. DOI:10.1093/nar/18.21.6231 |
 2006, Vol. 42
2006, Vol. 42