2. 广东中芯种业科技有限公司,广州 510642
2. Guangdong Zhongxin Breeding Technology Co. Ltd., Guangzhou 510642, China
瘦肉率指瘦肉质量占整个胴体质量的百分比[1],在《瘦肉型猪胴体性状测定技术规范NY/T825-2004》[2]中将瘦肉率定义为屠宰后左边胴体瘦肉重占皮、骨、肥肉和瘦肉重的百分比。瘦肉率是我国评价猪胴体质量等级的主要指标[1, 3],目前国内外胴体分级技术的主要方向是完善以瘦肉率为核心的胴体分级体系[4-5]。全国生猪遗传改良计划(2021—2035)要求建立胴体性状的测定标准[6],传统屠宰分割后称重测定瘦肉率的方法已不能满足计划要求。有研究表明,Fat-O-Meat’er-FOM、UltraFOM、Hennessy Grading Probe、VCS2000、AutoFom等仪器均能准确、快捷地估算瘦肉率[7-10]。
在现代育种工作中,动物模型通常被用来估计经济性状的方差组分和遗传力[11]。良好的拟合模型不仅可以保证方差组分的估计准确性,而且可以保证育种值估计的可靠性,进一步确保育种选种工作的稳步进行[12-13]。但是动物模型组成成分复杂,动物模型可以包含固定效应、加性遗传效应、母体效应或者各种环境效应等[14-16]。此外,在全国生猪遗传改良计划育种手册中我国种猪遗传评估方案明确建议在主要性状的遗传评估模型中加入窝效应[17],且相关研究表明,窝效应对体尺[18-19]、生长[20-22]和繁殖性状[23]的遗传评估准确性均有较大影响。本试验以广东中芯种业下属某核心场杜洛克群体为研究对象,评估瘦肉率性状的遗传参数及其与主要生长性状之间的关系,并分析窝效应对瘦肉率和主要生长性状的影响,旨在为瘦肉率性状的改良提供参考。
1 材料与方法 1.1 数据来源本试验以广东中芯种业科技有限公司下属某核心场杜洛克猪群体作为研究对象,选取2012—2022年场内校正115 kg瘦肉率(corrected 115 kg lean meat percentage,LMP)、校正115 kg日增重(corrected 115 kg daily gain,ADG)、校正115 kg背膘厚(corrected 115 kg backfat thickness,BFT)和校正115 kg眼肌面积(corrected 115 kg loin muscle area,LMA)等性状记录数据。其中LMP性状数据使用活体倒数3~4肋背膘厚数据精准估算得到。
1.2 数据处理和分析软件本研究利用Excel进行数据文件处理,按照DMU v6.0软件要求整理数据表型、系谱等,之后运用R v4.1.2软件对上述4个性状进行固定效应分析。
DMU v6.0软件[24]是一个全面的遗传评估工具,包含dmu1、dmuai、dmu4、dmu5、rjmc等模块,本研究采用的是dmuai模块,应用约束性最大似然法(restricted maximum likelihood, REML)估计方差组分,并估计模型内的所有效应值。
1.3 固定效应划分上述性状按测定年份划分为11个水平(2012—2022年,每年为1个水平);按测定季节划分为4个水平[25]: 春(3月11日-5月15日)、夏(5月16日-9月25日)、秋(9月26日-11月20日)、冬(11月21日-3月10日);性别划分为2个水平(公和母),按照出生胎次划分胎次效应,按照终测场划分场效应。
1.4 统计模型1.4.1 固定效应分析模型 利用R v4.1.2软件中的aov函数分析固定效应对杜洛克猪上述性状的影响[26]。上述各性状的固定效应方差分析模型如下:
| $ y_{i j k l}=\mu+y s_i+ { sex }_j+ { field }_k+ { parity }_l+e_{i j k l} $ |
其中,yijkl为性状表型值;μ为群体均值;ysi为测定年季效应;sexj为测定个体的性别效应;fieldk为终测场效应;parityl为出生胎次效应;eijkl为随机残差效应。
1.4.2 方差组分分析模型 本研究通过DMU v6.0软件计算方差组分,估计性状间的遗传相关,上述所有性状的方差组分分析均使用单/多性状模型,不考虑窝效应的模型如下:
| $ y=\boldsymbol{X} b+\boldsymbol{Z} a+e $ |
其中,y为性状表型值向量;b为固定效应向量(方差分析中有显著影响的效应);a为动物个体加性遗传效应向量,a~N(0, A σa2),σa2为个体加性遗传方差,A为加性遗传相关矩阵;X和Z分别为b和a对应的关联矩阵;e为残差向量e~N(0, Iσe2),σe2为残差方差,I为单位矩阵。
考虑窝效应的模型如下:
| $ y=\boldsymbol{X} b+\boldsymbol{Z}_1 a+\boldsymbol{Z}_2 l+e $ |
其中,y为性状表型值向量;b为固定效应向量(方差分析中有显著影响的效应);a为动物个体加性遗传效应向量,a~N(0, A σa2),σa2为个体加性遗传方差,A为加性遗传相关矩阵;l为个体出生时所在窝的窝效应向量,l~N(0, I σl2),σl2为个体窝效应方差;X、Z1和Z2分别为b、a和l对应的关联矩阵;e为残差向量,e~N(0, Iσe2),σe2为残差方差,I为单位矩阵。个体窝效应记录是由其母亲个体号加上分娩年月组成。
1.5 遗传趋势计算用DMU v6.0软件的DMU4模块计算LMP性状的育种值,并对育种值均值随终测年份变化的趋势结果进行可视化。
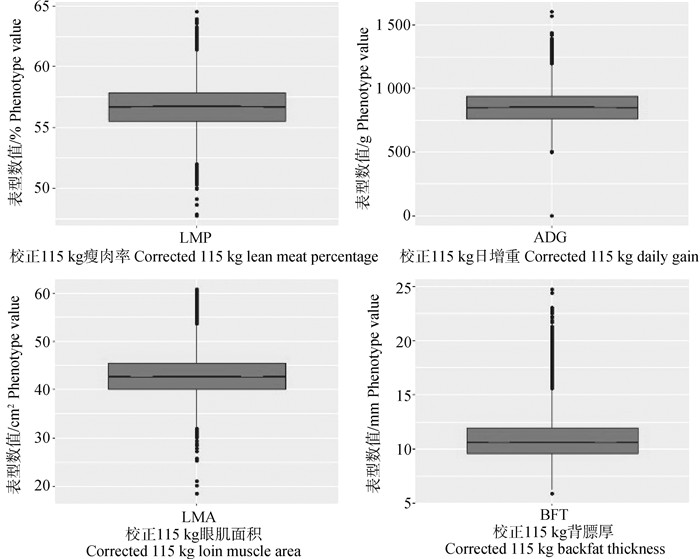
2 结果 2.1 各性状的描述性统计上述所有性状表型值统计量见表 1与图 1。上述所有性状的表型记录数量均达到20 000条以上,其中LMP性状数据量达到了26 392条,平均数为56.69%,标准差为1.77,异常值比例为0.25%,变异系数相对偏小为3.12%,而ADG、BFT和LMA性状的表型变异系数变化范围为9.43%~18.43%,相对偏大。
|
|
表 1 各性状的基本统计量 Table 1 Basic statistics of each trait |
|
图 1 各性状表型值分布箱线图 Fig. 1 Box diagram of phenotypic values distribution of each trait |
由表 2可知,年季效应、性别效应、场效应、胎次效应对LMP、ADG、BFT和LMA等性状的影响均达到了极显著水平,可用于遗传方差统计模型。
|
|
表 2 固定效应显著性检验 Table 2 Significance test of fixed effects |
由表 3可知,本研究在遗传评估模型中不考虑窝效应时,LMP、ADG、BFT和LMA性状的的遗传力估计分别为0.45±0.017、0.33±0.017、0.40±0.017、0.45±0.017,均属于中高等遗传力。但是,当本研究中将窝效应作为随机效应加入遗传评估模型后(表 4),估计LMP、ADG、BFT、LMA性状的遗传力分别为0.34±0.019、0.19±0.017、0.30±0.019、0.35±0.019。此外,LMP、ADG、BFT和LMA性状的窝效应在总体方差中的比重分别为0.15、0.21、0.15和0.14,由此可见窝效应对上述性状均有较大影响,其中对ADG性状影响最大。
|
|
表 3 不考虑窝效应各性状方差组分和遗传力 Table 3 Variance components and heritability of each trait without considering the litter effect |
|
|
表 4 考虑窝效应各性状方差组分和遗传力 Table 4 Variance components and heritability of each trait with considering the litter effect |
由表 5可知,本研究在遗传评估模型中不考虑窝效应时,LMP与ADG和LMA性状的遗传相关分别为-0.11和0.94,表型相关分别为-0.048和0.93,可以发现LMP与LMA性状均呈极显著正相关。但是本研究中将窝效应考虑进遗传评估模型后(表 6),发现估算LMP与ADG和LMA的遗传相关分别为-0.13和0.94,表型相关分别为-0.031和0.800,同样可以发现,LMP与LMA性状均呈极显著正相关,而LMP与ADG性状之间的遗传相关和表型相关系数均较小。
|
|
表 5 不考虑窝效应的各性状间遗传和表型相关 Table 5 Genetic and phenotypic correlations among traits without considering the litter effect |
|
|
表 6 考虑窝效应的各性状间遗传和表型相关 Table 6 Genetic and phenotypic correlations among traits with considering the litter effect |
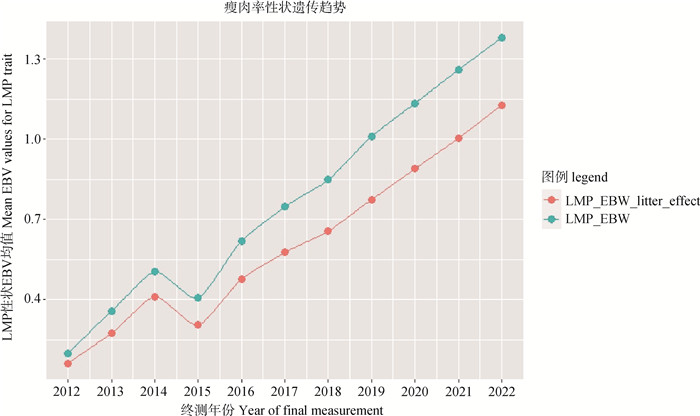
由图 2可知,杜洛克群体在2012—2022年的选育过程中,LMP性状年平均EBV呈上升趋势,说明该群体LMP性状受到了定向选择。
|
图 2 瘦肉率性状遗传趋势 Fig. 2 Genetic trend of lean meat percentage trait |
本研究中,杜洛克猪的LMP、ADG、BFT和LMA性状不考虑窝效应作为随机效应时,估计的遗传力分别为0.45±0.017、0.33±0.017、0.40±0.017和0.45±0.017,略低于Gilbert等[27]、Déru等[28]、Homma等[29]和Cabling等[30]的研究结果,高于Zhou等[31]、Seong等[32]和黄叶[33]的研究结果。此外,如果在上述性状的遗传评估模型中考虑窝效应后,发现上述性状的估计遗传力分别为0.34±0.019、0.19±0.017、0.30±0.019、0.35±0.019,高于Davoli等[34]的研究结果,略低于Knapp等[35]的研究结果。上述结果说明,本研究结果在已知估计遗传力的范围内,可以为目标群体的遗传评估提供参考,且上述结果差异可能与研究群体的品种、遗传结构、遗传评估模型、运算软件、表型和系谱处理等有关。此外,本研究发现LMP与ADG性状的遗传相关系数较小,但是与LMA性状呈极显著正相关。进一步解释了各国将LMA性状作为辅助性状选育瘦肉率的原因[36-37],同时也说明影响LMA性状的关键基因或位点可能是一因多效或者影响LMP性状的关键基因或位点与LMA处于强连锁状态。
本研究中,LMP性状的遗传趋势分析结果表示该杜洛克群体在2012—2014年中有短暂平缓的上升趋势,在2014—2015年呈下降趋势,但是在2015—2022年呈明显的上升趋势,但是遗传趋势上升速度较平缓。LMP作为目前生猪胴体分级的主要指标,直接影响生猪销售价格,本研究群体根据表型选育的方法所得遗传进展较缓慢,未能满足消费市场对高瘦肉率的需求。伴随基因组测序技术和数据分析手段的日益发展,使用基因组选择技术来选育LMP性状可能会提高个体的选择准确性,实现早期选育,加快遗传进展[38-40]。
3.2 窝效应对瘦肉率和主要生长性状的影响分析本研究结果表明,LMP、ADG、BFT和LMA性状的窝效应在总体方差中的比重分别为0.15、0.21、0.15、0.14,与Knapp等[35]的研究结果基本一致,略高于Dong等[11]和杨涛等[21]的研究结果。上述结果表明,不考虑窝效应的遗传评估模型高估了性状的遗传力,尤其高估了ADG性状的遗传力。因此,考虑窝效应对LMP、ADG、BFT和LMA性状进行遗传评估具有更好的拟合效果,但是窝效应的准确统计在实际生产中仍然是需要解决的大问题。实际生产中,由于产后母猪的带仔能力和仔猪身体情况差异,经常会发生寄入、寄出情况。对于全同胞仔猪而言,如果发生寄入、寄出情况,窝效应就不同,不能简单通过系谱数据分析得出。因此,为获得更准确的LMP估计育种值,应该在仔猪饲养过程中尽可能减少仔猪的寄养,尽量保证窝效应记录的准确性。此外,其他因素如母体效应、基因和环境互作效应对LMP性状的影响研究可能会进一步提高性状遗传评估准确性,但相关证明有待下一步开展。
4 结论上述结果说明,该杜洛克群体的LMP、ADG、BFT和LMA的遗传力均属于中等遗传力,且受窝效应影响较大。在遗传评估模型中考虑窝效应作为随机效应进一步提高了上述性状的拟合效果,增加了遗传评估的准确性,此外其他未考虑效应如母体遗传效应等对上述性状的影响仍需进一步探讨。遗传相关结果表示,LMP与ADG性状的遗传相关系数较小,但是与LMA性状呈极显著正相关,可见在相同体重范围情况下,LMA越大,对LMP有正向选育效果。在该群体中,LMP性状呈上升的遗传趋势,说明瘦肉率选育工作有所成效。
| [1] |
中华人民共和国农业农村部. NY/T 3380-2018猪肉分级[S]. 北京: 中国标准出版社, 2018. Ministry of Agriculture and Rural Affairs of the People's Republic of China. NY/T 3380-2018 Grading standard for pork[S]. Beijing: Standards Press of China, 2018. (in Chinese) |
| [2] |
中华人民共和国农业部. NY/T 825-2004瘦肉型猪胴体性状测定技术规范[S]. 北京: 中国农业出版社, 2004. Ministry of Agriculture of the PRC. NY/T 825-2004 Technical regulation for testing of carcass traits in lean-type pig[S]. Beijing: China Agriculture Press, 2004. (in Chinese) |
| [3] |
骆先虎, 王国平. 猪胴体分级技术初探[J]. 畜牧与兽医, 2012, 44(5): 40-43. LUO X H, WANG G P. A first look at pig carcass grading techniques[J]. Animal Husbandry & Veterinary Medicine, 2012, 44(5): 40-43. (in Chinese) |
| [4] |
DELGADO-PANDO G, ALLEN P, TROY D J, et al. Objective carcass measurement technologies: Latest developments and future trends[J]. Trends Food Sci Technol, 2021, 111: 771-782. DOI:10.1016/j.tifs.2020.12.016 |
| [5] |
王继鹏, 方永卫, 翟海港, 等. 生猪采购瘦肉率方程适用性分析[J]. 肉类工业, 2016(12): 20-23. WANG J P, FANG Y W, ZHAI H G, et al. Applicability analysis of lean meat percentage equation for live pigs purchase[J]. Meat Industry, 2016(12): 20-23. DOI:10.3969/j.issn.1008-5467.2016.12.007 (in Chinese) |
| [6] |
全国生猪遗传改良计划(2021—2035年)[J]. 猪业观察, 2021(3): 6-9. National genetic improvement plan for pigs (2021-2035)[J]. Swine Industry Outlook, 2021(3): 6-9. (in Chinese) |
| [7] |
FORTIN A, TONG A K W, ROBERTSON W M. Evaluation of three ultrasound instruments, CVT-2, UltraFom 300 and AutoFom for predicting salable meat yield and weight of lean in the primals of pork carcasses[J]. Meat Sci, 2004, 68(4): 537-549. DOI:10.1016/j.meatsci.2004.05.006 |
| [8] |
FONT I FURNOLS M, GISPERT M. Comparison of different devices for predicting the lean meat percentage of pig carcasses[J]. Meat Sci, 2009, 83(3): 443-446. DOI:10.1016/j.meatsci.2009.06.018 |
| [9] |
ENGEL B, LAMBOOIJ E, BUIST W G, et al. Lean meat prediction with HGP, CGM and CSB-Image-Meater, with prediction accuracy evaluated for different proportions of gilts, boars and castrated boars in the pig population[J]. Meat Sci, 2012, 90(2): 338-344. DOI:10.1016/j.meatsci.2011.07.020 |
| [10] |
LOHUMI S, WAKHOLI C, BAEK J H, et al. Erratum to: Nondestructive estimation of lean meat yield of south Korean pig carcasses using machine vision technique[J]. Food Sci Anim Resour, 2019, 39(3): 520. DOI:10.5851/kosfa.2019.e47 |
| [11] |
DONG L S, TAN C, CAI G Y, et al. Estimates of variance components and heritability using different animal models for growth, backfat, litter size, and healthy birth ratio in Large White pigs[J]. Can J Anim Sci, 2020, 100(2): 330-336. DOI:10.1139/cjas-2019-0136 |
| [12] |
ALAM M, CHANG H K, LEE S S, et al. Genetic analysis of major production and reproduction traits of Korean duroc, landrace and Yorkshire pigs[J]. Animals (Basel), 2021, 11(5): 1321. |
| [13] |
HERRERA-CÁCERES W, RAGAB M, SÁNCHEZ J P. Indirect genetic effects on the relationships between production and feeding behaviour traits in growing Duroc pigs[J]. Animal, 2020, 14(2): 233-242. DOI:10.1017/S1751731119002179 |
| [14] |
HENDERSON C R. Theoretical basis and computational methods for a number of different animal models[J]. J Dairy Sci, 1988, 71(S2): 1-16. |
| [15] |
AHMAD S F, GAUR G K, PANDA S, et al. Bayesian analysis reveals the influence of maternal effect on pre-weaning body weights in Landlly piglets[J]. Zygote, 2022, 30(5): 625-632. DOI:10.1017/S0967199422000065 |
| [16] |
KAVLAK A T, STRANDÉN I, LIDAUER M H, et al. Estimation of social genetic effects on feeding behaviour and production traits in pigs[J]. Animal, 2021, 15(3): 100168. DOI:10.1016/j.animal.2020.100168 |
| [17] |
全国畜牧总站. 全国生猪遗传改良计划工作手册[M]. 北京: 中国农业大学出版社, 2013: 57-58. National Animal Husbandry Services. Workbook of the national pig genetic improvement program[M]. Beijing: China Agricultural University Press, 2013: 57-58. (in Chinese) |
| [18] |
叶健, 胡晓湘, 屈胜丽, 等. 大白猪体型性状的遗传参数及其与生产性能的关系[J]. 中国畜牧杂志, 2016, 52(19): 6-8, 45. YE J, HU X X, QU S L, et al. Estimation of genetic parameters of type traits and it's correlation with production traits in large white pigs[J]. Chinese Journal of Animal Science, 2016, 52(19): 6-8, 45. (in Chinese) |
| [19] |
OGAWA S, YAZAKI N, OHNISHI C, et al. Maternal effect on body measurement and meat production traits in purebred Duroc pigs[J]. J Anim Breed Genet, 2021, 138(2): 237-245. DOI:10.1111/jbg.12505 |
| [20] |
周子文, 付璐, 孟庆利, 等. 利用后裔测定验证大白猪基因组选择实施效果研究[J]. 畜牧兽医学报, 2020, 51(10): 2367-2377. ZHOU Z W, FU L, MENG Q L, et al. Using progeny testing to evaluate the efficiency of genomic selection in large white pigs[J]. Acta Veterinaria et Zootechnica Sinica, 2020, 51(10): 2367-2377. DOI:10.11843/j.issn.0366-6964.2020.10.005 (in Chinese) |
| [21] |
杨涛, 张敏婕, 徐然, 等. 应用BLUP方法对猪繁殖性状和生长性状遗传评估的研究[J]. 中国畜牧兽医, 2022, 49(8): 2971-2981. YANG T, ZHANG M J, XU R, et al. Study on genetic evaluation of reproductive and growth traits in pigs by BLUP method[J]. China Animal Husbandry & Veterinary Medicine, 2022, 49(8): 2971-2981. DOI:10.16431/j.cnki.1671-7236.2022.08.013 (in Chinese) |
| [22] |
LEE H L, LIN M Y, WANG H S, et al. Direct-maternal genetic parameters for litter size and body weight of piglets of a new black breed for the Taiwan black hog market[J]. Animals (Basel), 2022, 12(23): 3295. |
| [23] |
叶健, 蔡更元, 刘德武, 等. 初生和有效乳头数与生产性状之间的相关性分析[J]. 中国畜牧杂志, 2018, 54(8): 49-51, 55. YE J, CAI G Y, LIU D W, et al. Correlation between teat number and other production traits[J]. Chinese Journal of Animal Science, 2018, 54(8): 49-51, 55. DOI:10.19556/j.0258-7033.2018-08-049 (in Chinese) |
| [24] |
MADSEN P, SORENSEN P, SU G, et al. DMU-A package for analyzing multivariate mixed models[C]//8th World Congress on Genetics Applied to Livestock Production. Brazil: Minas Gerais, 2006.
|
| [25] |
张世轩. 全球增暖背景下中国四季的划分及与夏季降水的关系[D]. 兰州: 兰州大学, 2013. ZHANG S X. The identification of four seasons in China and its relationship with summer rainfall under global warming[D]. Lanzhou: Lanzhou University, 2013. (in Chinese) |
| [26] |
周辅臣, 叶健, 董林松, 等. 杜洛克猪肌内脂肪含量性状遗传参数估计及其与主要生长性状的关系[J]. 中国畜牧杂志, 2023, 1-8. ZHOU F C, YE J, DONG L S, et al. Genetic parameter estimation of intramuscular fat content and its relationship with main growth traits in Duroc pigs[J]. Chinese Journal of Animal Science, 2023, 1-8. DOI:10.19556/j.0258-7033.20220907-01 (in Chinese) |
| [27] |
GILBERT H, BIDANEL J P, GRUAND J, et al. Genetic parameters for residual feed intake in growing pigs, with emphasis on genetic relationships with carcass and meat quality traits[J]. J Anim Sci, 2007, 85(12): 3182-3188. DOI:10.2527/jas.2006-590 |
| [28] |
DÉRU V, BOUQUET A, HASSENFRATZ C, et al. Impact of a high-fibre diet on genetic parameters of production traits in growing pigs[J]. Animal, 2020, 14(11): 2236-2245. DOI:10.1017/S1751731120001275 |
| [29] |
HOMMA C, HIROSE K, ITO T, et al. Estimation of genetic parameter for feed efficiency and resilience traits in three pig breeds[J]. Animal, 2021, 15(11): 100384. DOI:10.1016/j.animal.2021.100384 |
| [30] |
CABLING M M, KANG H S, LOPEZ B M, et al. Estimation of genetic associations between production and meat quality traits in Duroc pigs[J]. Asian-Australas J Anim Sci, 2015, 28(8): 1061-1065. DOI:10.5713/ajas.14.0783 |
| [31] |
ZHOU S P, DING R R, MENG F M, et al. A meta-analysis of genome-wide association studies for average daily gain and lean meat percentage in two Duroc pig populations[J]. BMC Genomics, 2021, 22(1): 12. DOI:10.1186/s12864-020-07288-1 |
| [32] |
SEONG H S, KIM Y S, SA S J, et al. Genetic parameter estimation and genome-wide association analysis of social genetic effects on average daily gain in purebreds and crossbreds[J]. Animals, 2022, 12(17): 2300. DOI:10.3390/ani12172300 |
| [33] |
黄叶. 大白猪胴体性状全基因组关联分析及遗传参数估计[D]. 南宁: 广西大学, 2020. HUANG Y. Genome wide association analysis and genetic parameter estimation of carcass traits in Yorkshire pigs[D]. Nanning: Guangxi University, 2020. (in Chinese) |
| [34] |
DAVOLI R, CATILLO G, SERRA A, et al. Genetic parameters of backfat fatty acids and carcass traits in Large White pigs[J]. Animal, 2019, 13(5): 924-932. DOI:10.1017/S1751731118002082 |
| [35] |
KNAPP P, WILLAM A, SÖLKNER J. Genetic parameters for lean meat content and meat quality traits in different pig breeds[J]. Livest Prod Sci, 1997, 52(1): 69-73. DOI:10.1016/S0301-6226(97)00120-6 |
| [36] |
FONT-I-FURNOLS M, AČG ANDEK-POTOKAR M, DAUMAS G, et al. Comparison of national ZP equations for lean meat percentage assessment in SEUROP pig classification[J]. Meat Sci, 2016, 113: 1-8. DOI:10.1016/j.meatsci.2015.11.004 |
| [37] |
AYUSO D, GONZÁLEZ A, HERNÁNDEZ F, et al. Prediction of carcass composition, ham and foreleg weights, and lean meat yields of Iberian pigs using ultrasound measurements in live animals1[J]. J Anim Sci, 2013, 91(4): 1884-1892. DOI:10.2527/jas.2012-5357 |
| [38] |
MISZTAL I, LOURENCO D, LEGARRA A. Current status of genomic evaluation[J]. J Anim Sci, 2020, 98(4): skaa101. DOI:10.1093/jas/skaa101 |
| [39] |
SAMORÈ A B, BUTTAZZONI L, GALLO M, et al. Genomic selection in a pig population including information from slaughtered full sibs of boars within a sib-testing program[J]. Animal, 2015, 9(5): 750-759. |
| [40] |
AZEVEDO C F, NASCIMENTO M, SILVA F F, et al. Comparison of dimensionality reduction methods to predict genomic breeding values for carcass traits in pigs[J]. Genet Mol Res, 2015, 14(4): 12217-12227. |
(编辑 郭云雁)



